作者按
国内对于单细胞测序相关的中文教程确实不够全面,当然NCBI官网给的上传教程也比较详细了,所以变成了会者不难。本教程你现在可能用不上,但是你如果做单细胞测序,那么未来你一定会用上,建议收藏。
在这里,我们将演示如何将测序文件完整上传到NCBI上。本教程首发于单细胞最好的中文教程,未经授权许可,禁止转载。
全文字数|预计阅读时间: 3500|5min
——星夜老师
1. 注册NCBI账户
我们首先打开SRA的上传官网:https://submit.ncbi.nlm.nih.gov/subs/sra/,注册一个账户
注意
不能使用163,qq邮箱之类的,可能会收不到邮件
2. 新建SRA提交
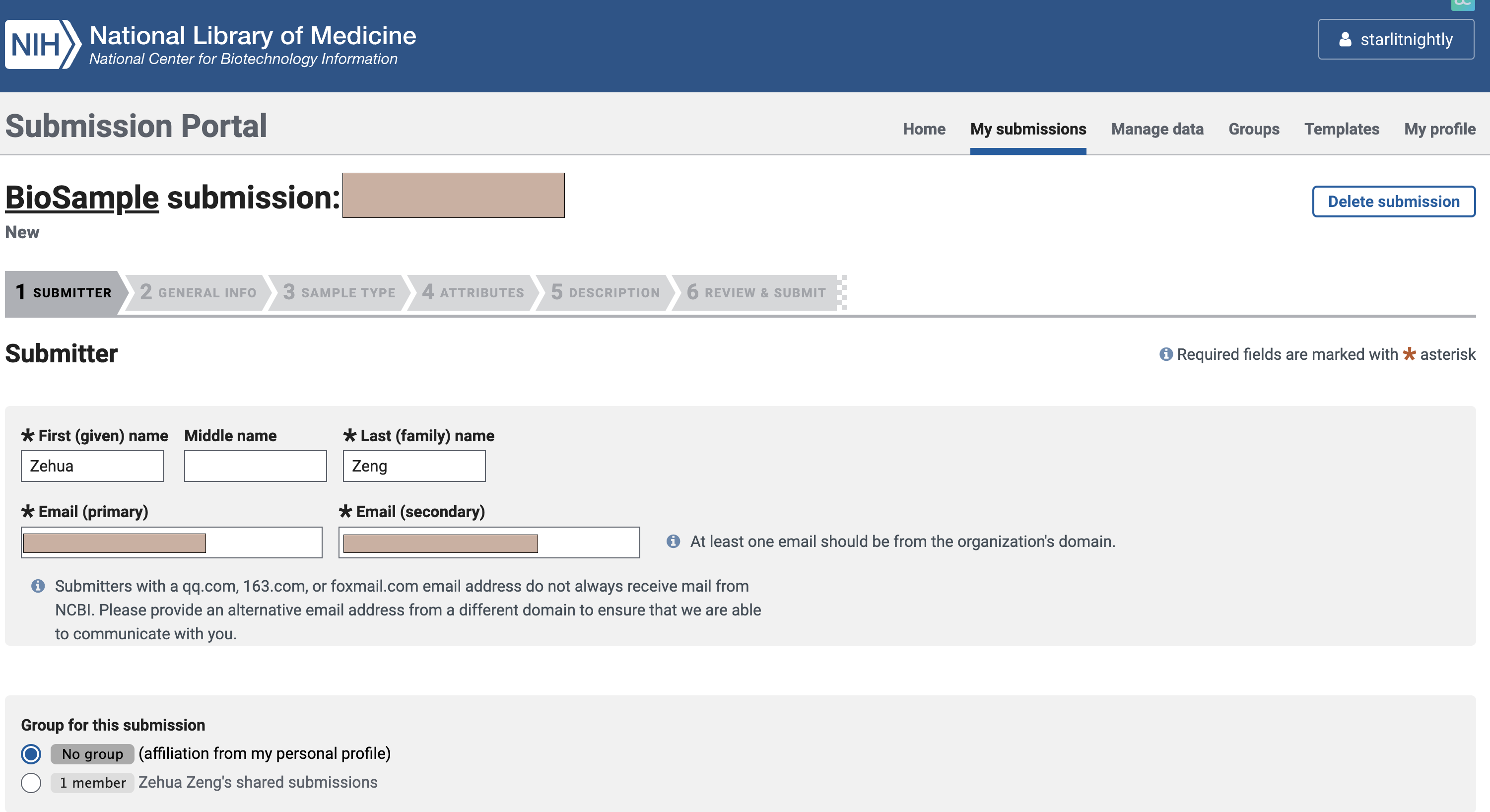
2.1 选择Biosample
我们首先需要准备biosample,这个是需要ncbi官网审核的,每一个biosample代表了一个真实的样本。
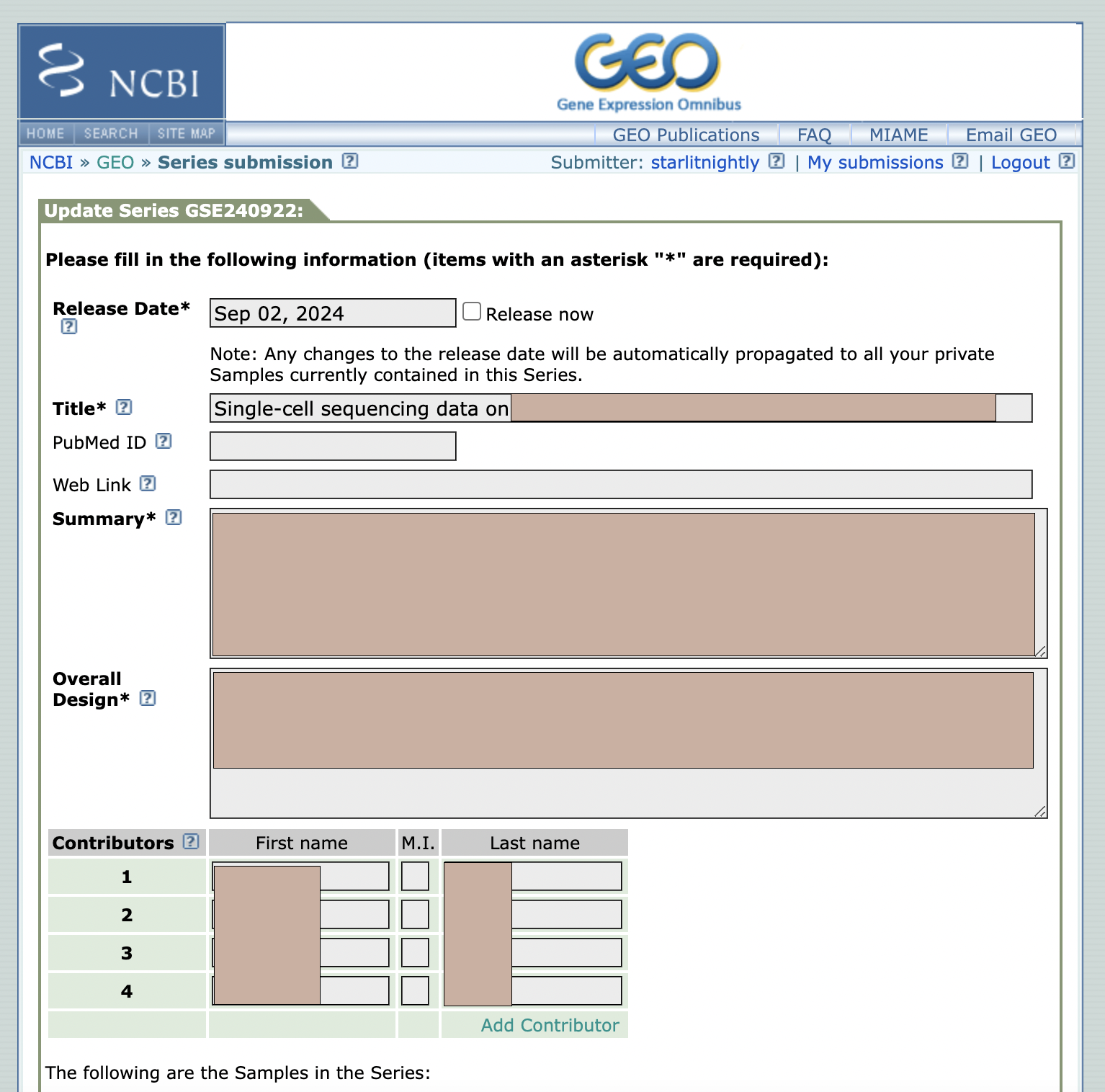
2.2 填写信息
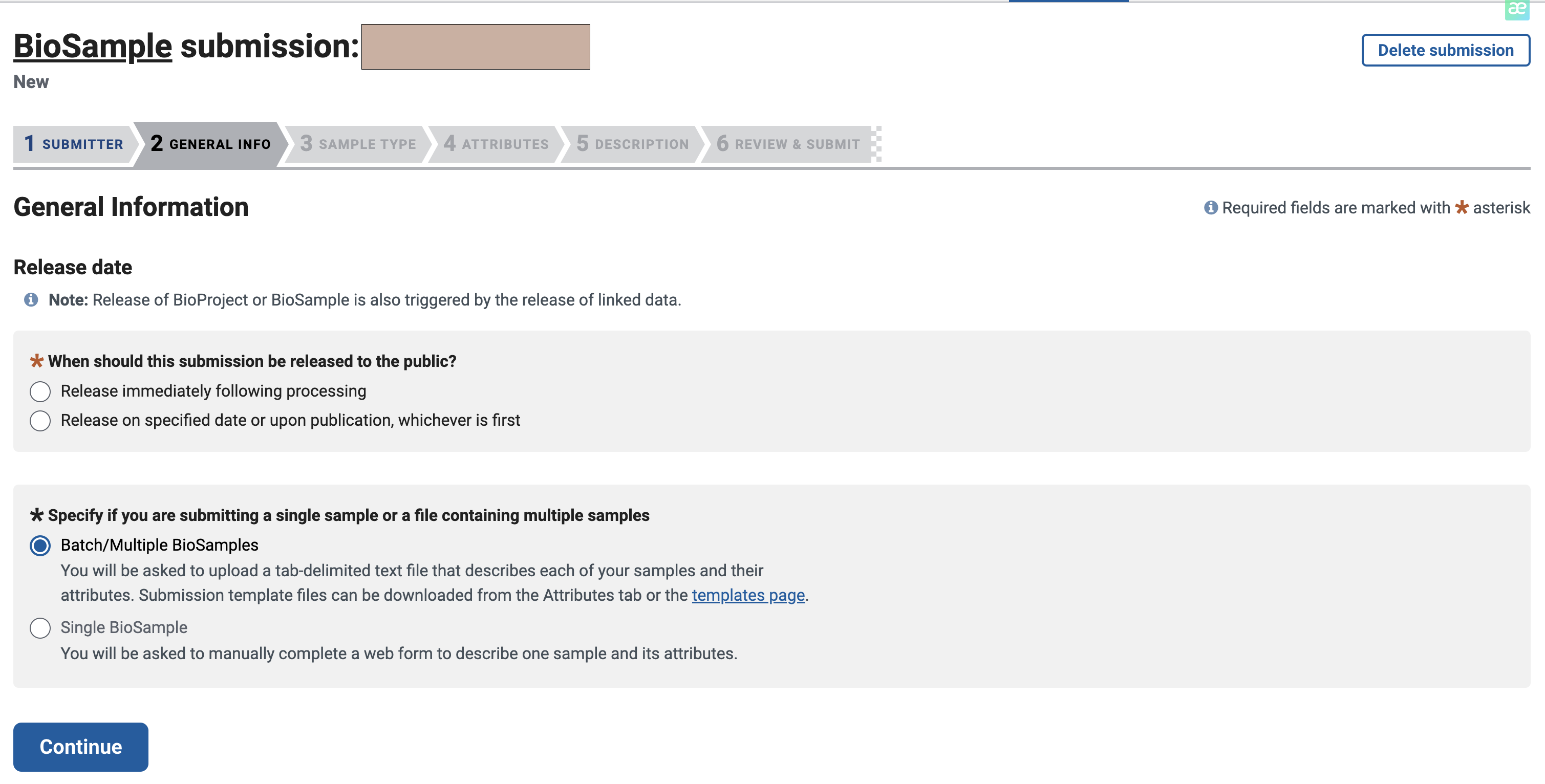
一般来说,我们可以指定一个数据的释放日期,我估计一年的时间论文应该能发出去,所以设置到了明年同一时间。
下拉选择人类资源Human
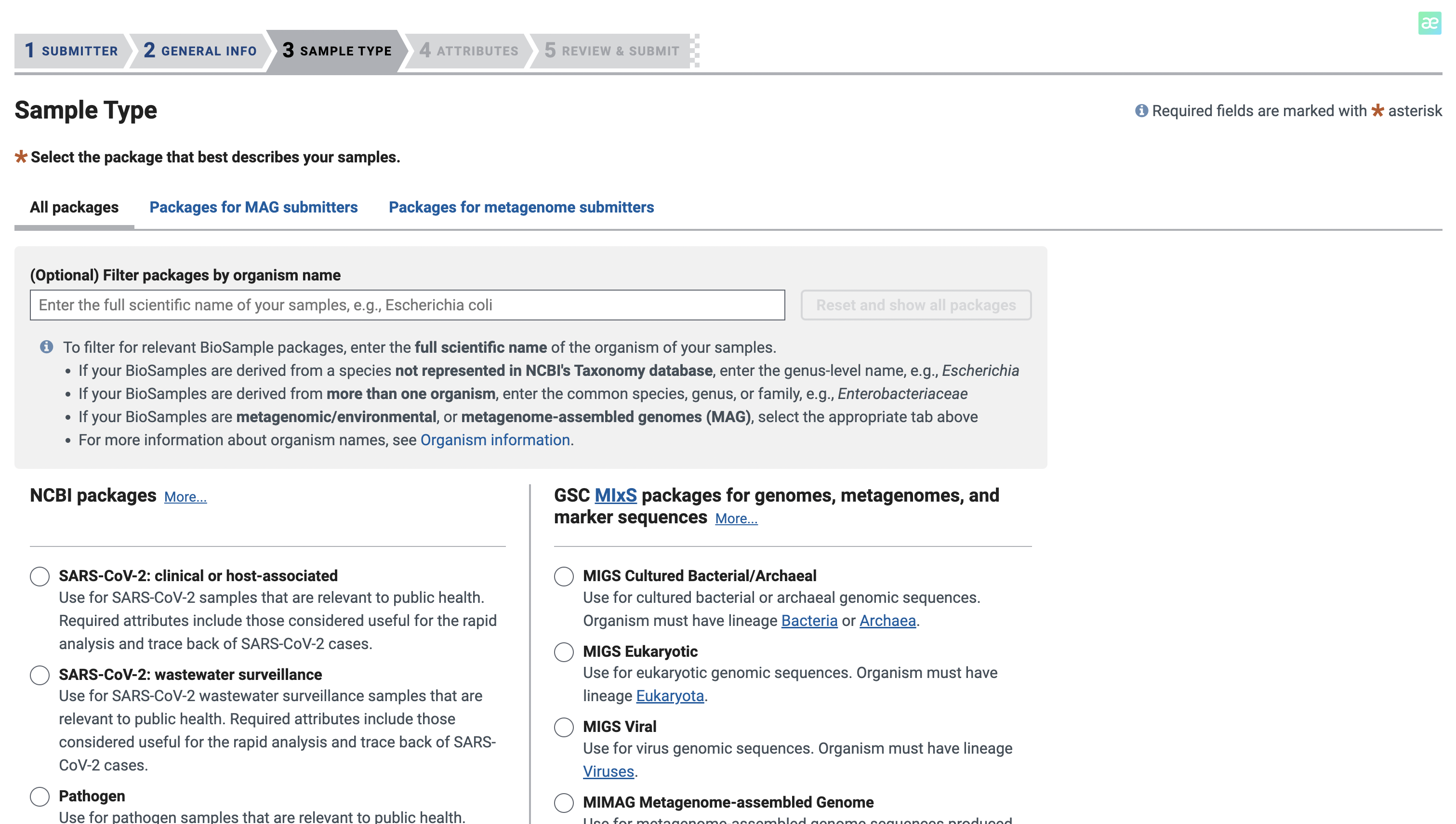
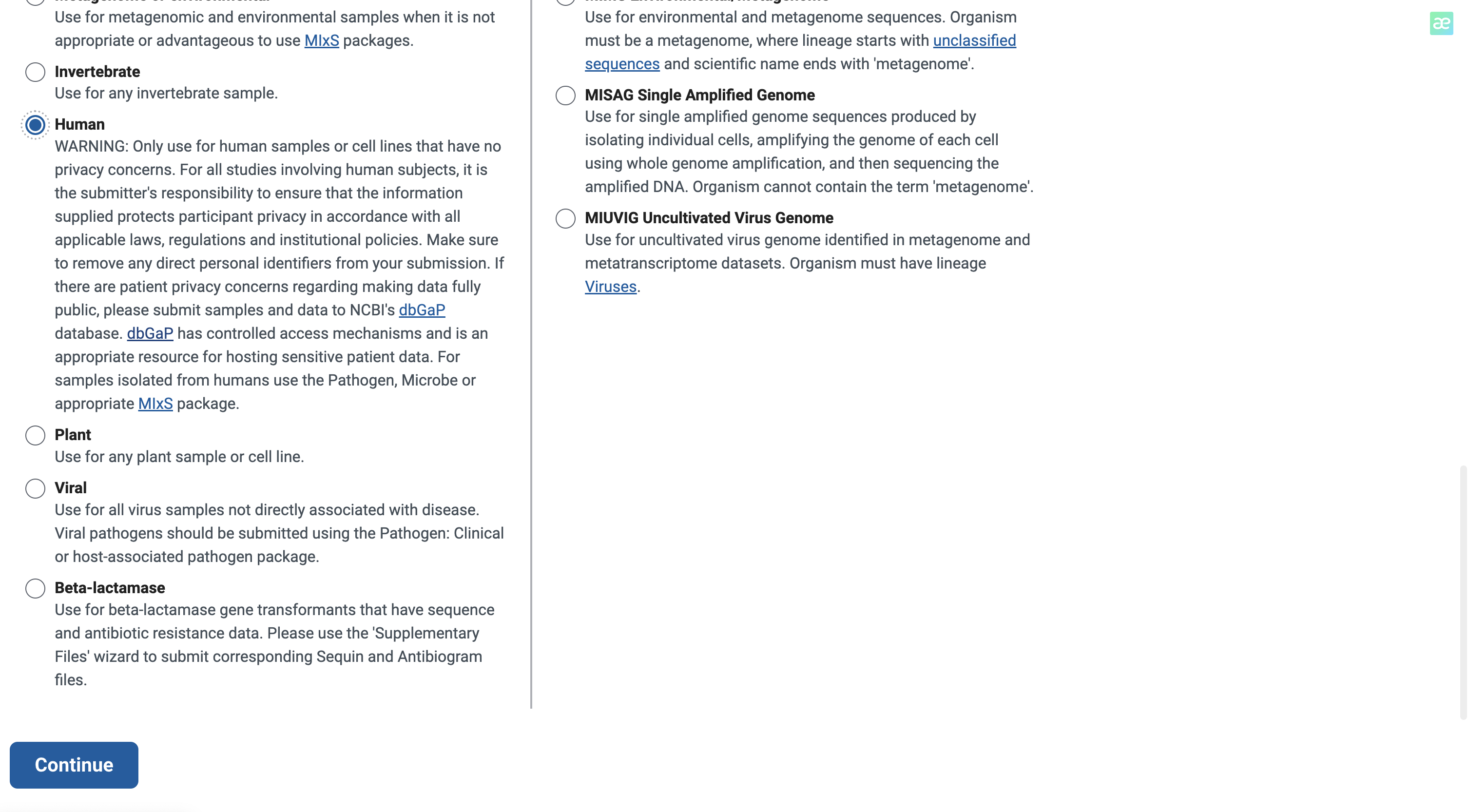
在这里,我们选择文件上传的方式进行填写
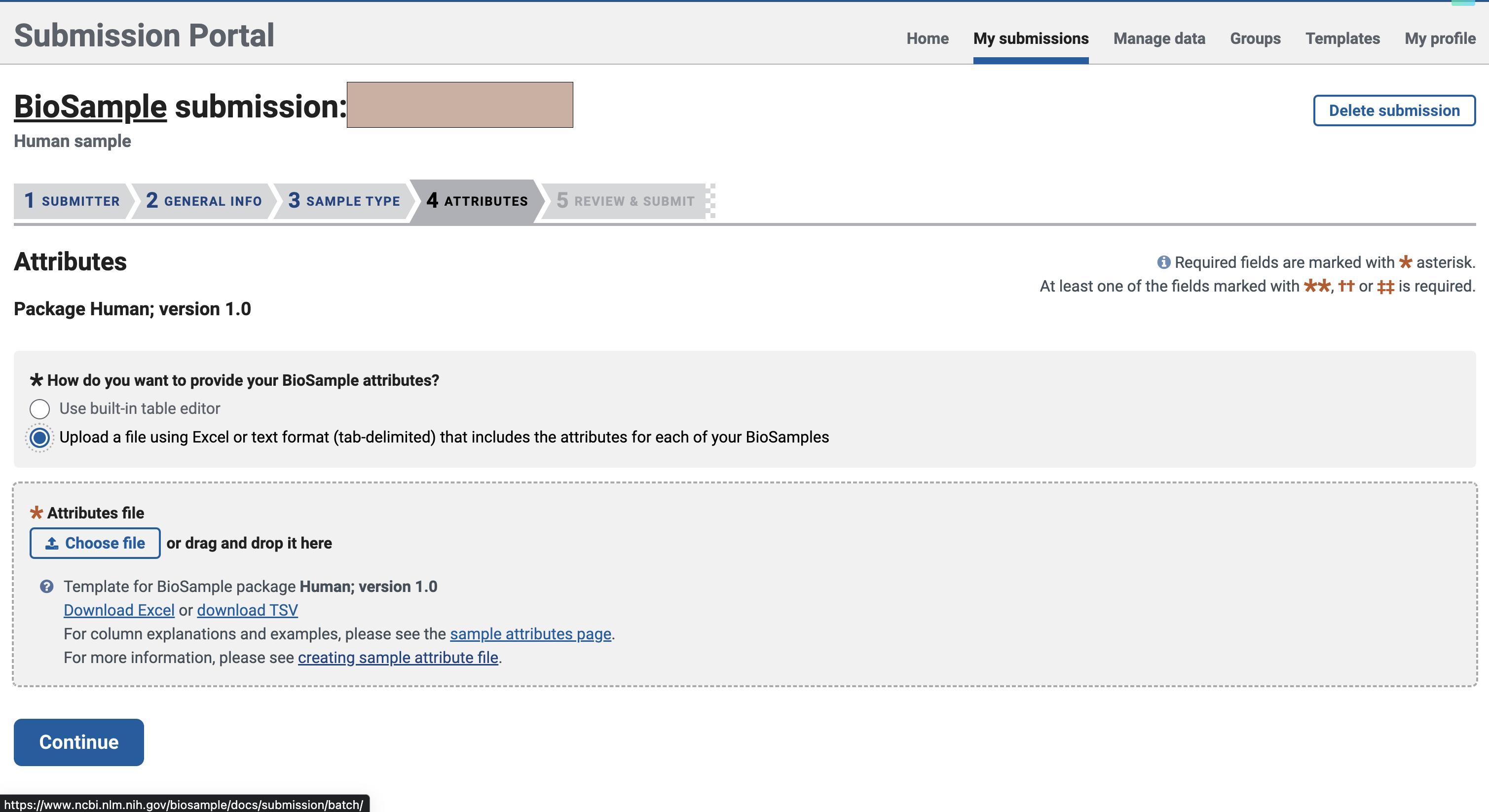
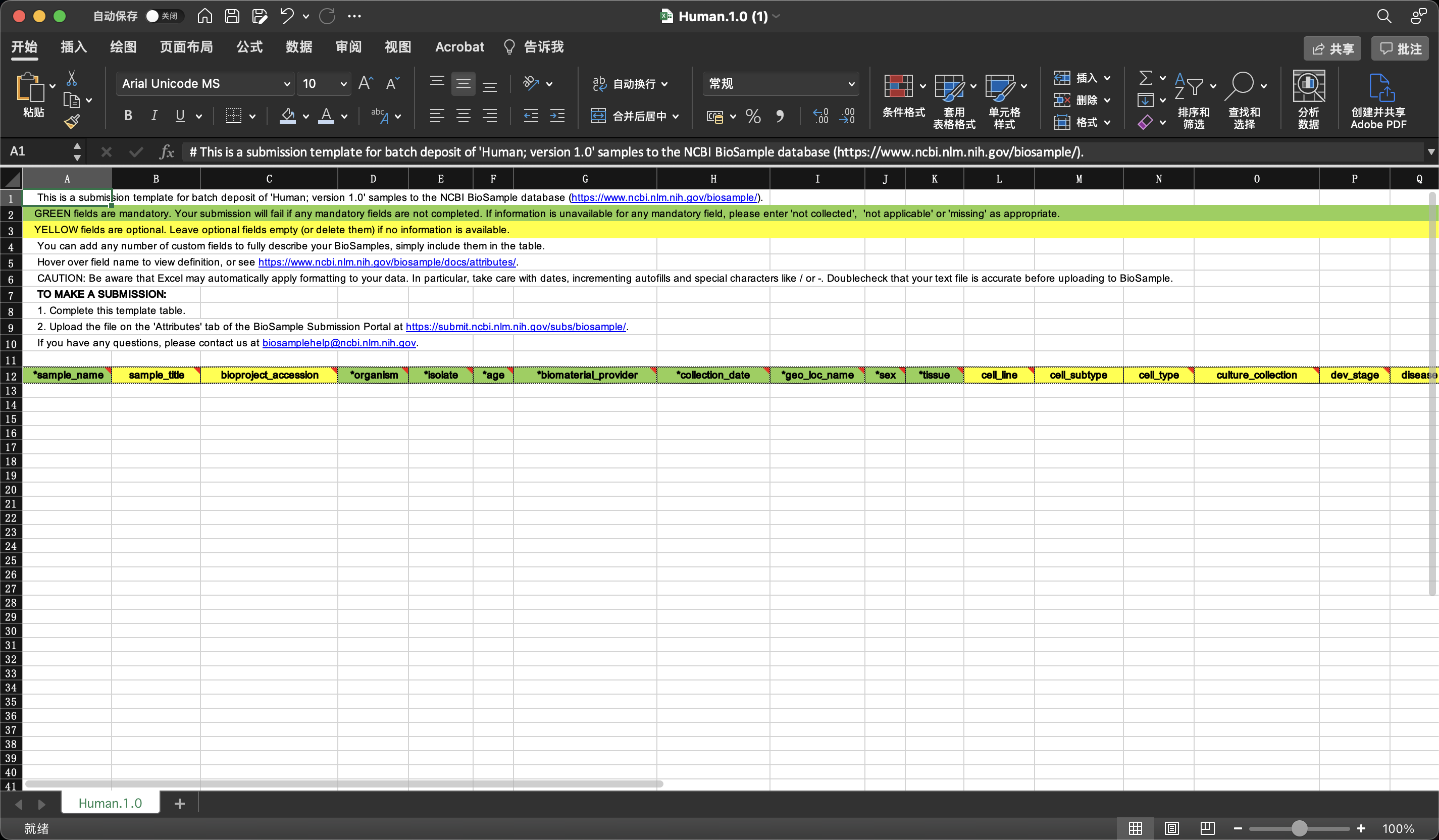
文件大概长这个样,绿色是必填项,黄色是可选项,你也可以添加自己的属性。不过需要注意的是,对于不同的sample_name,后面的属性不能完全一致,即使是同一种病,建议把病人来源标上,这样就能不重复了。
我们提交后出现这个页面,等待管理员审核即可。
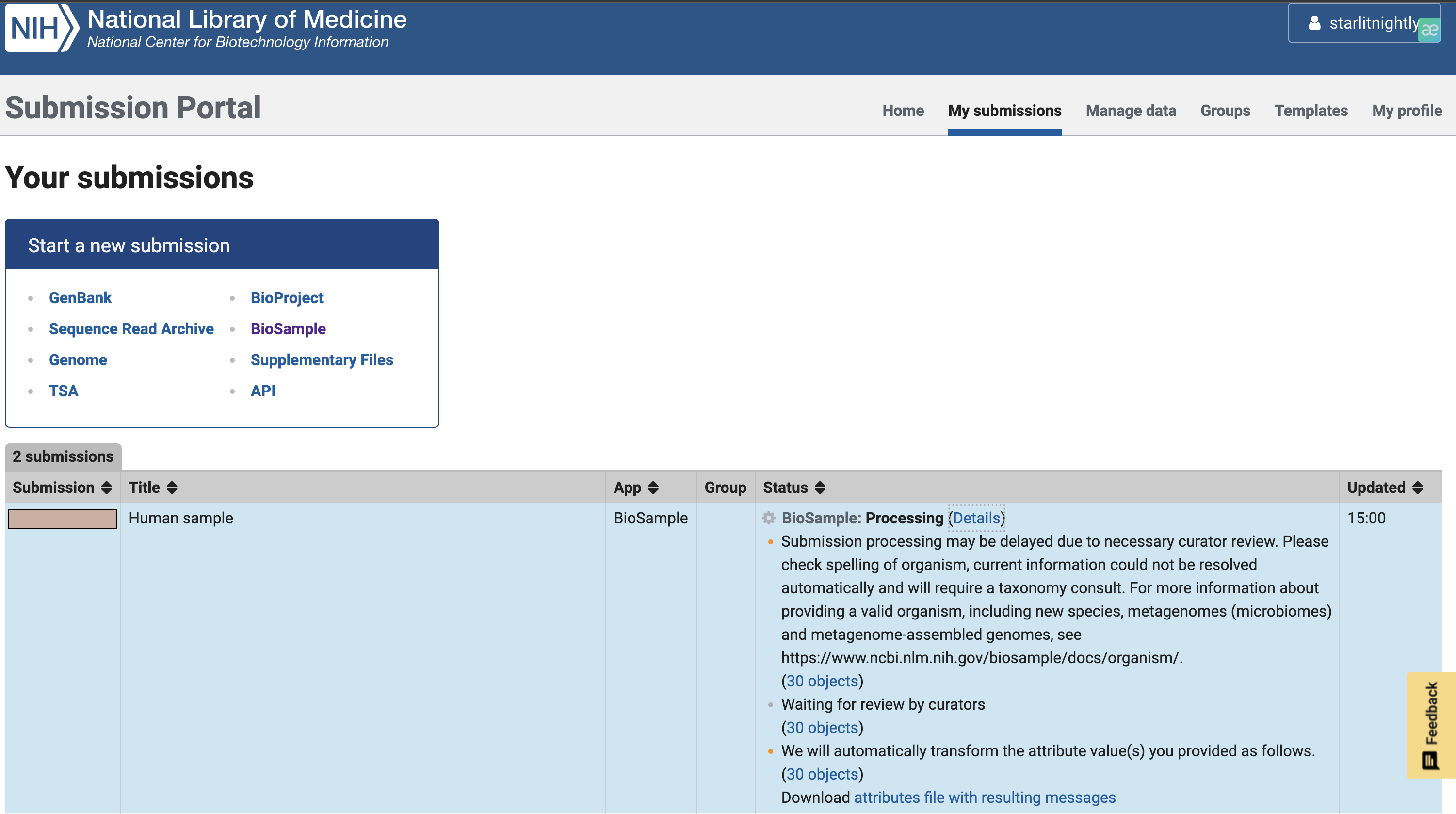
3. 上传fastq
3.1 biosample获取
经过三天的等待,我们的fastq的上传审核终于完成了
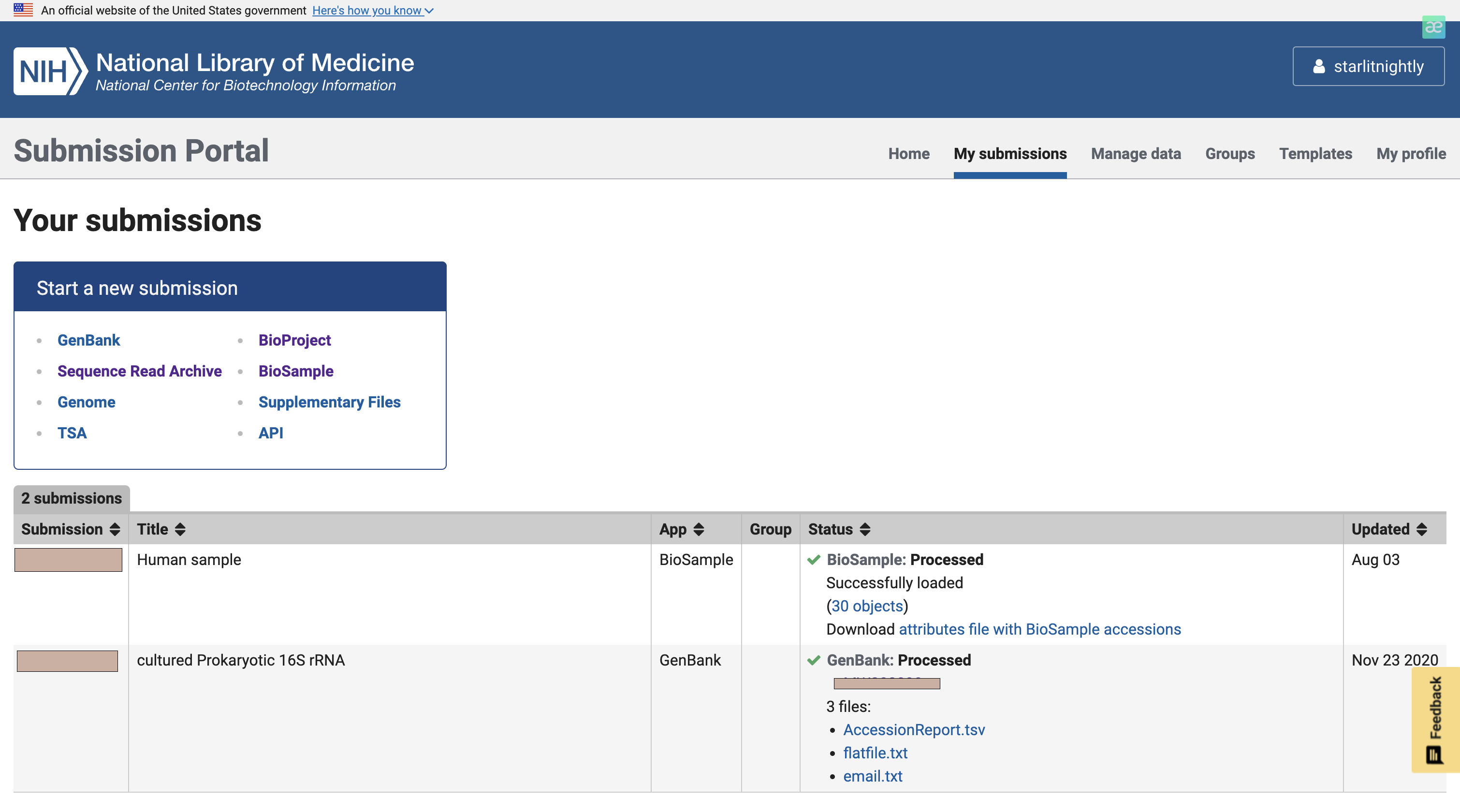
我们点击manage data发现多了30个biosample可以进行上传,这里的Accession就是我们的biosample的id,每个样本唯一。
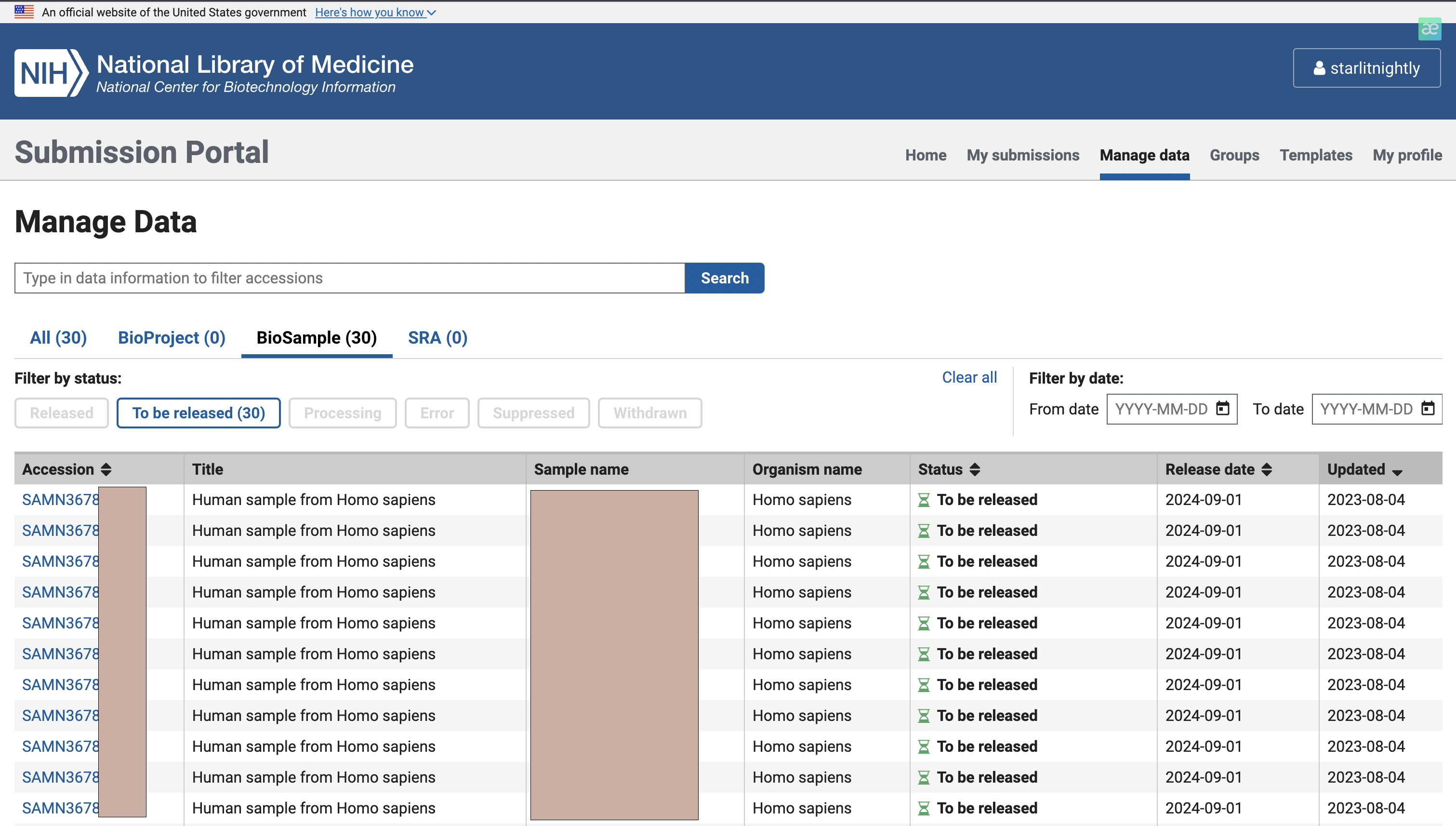
3.2 上传SRA数据
我们点击上一个页面的Sequence Read Archive,准备上传fastq
由于我的数据在服务器上,所以我们选择命令行上传
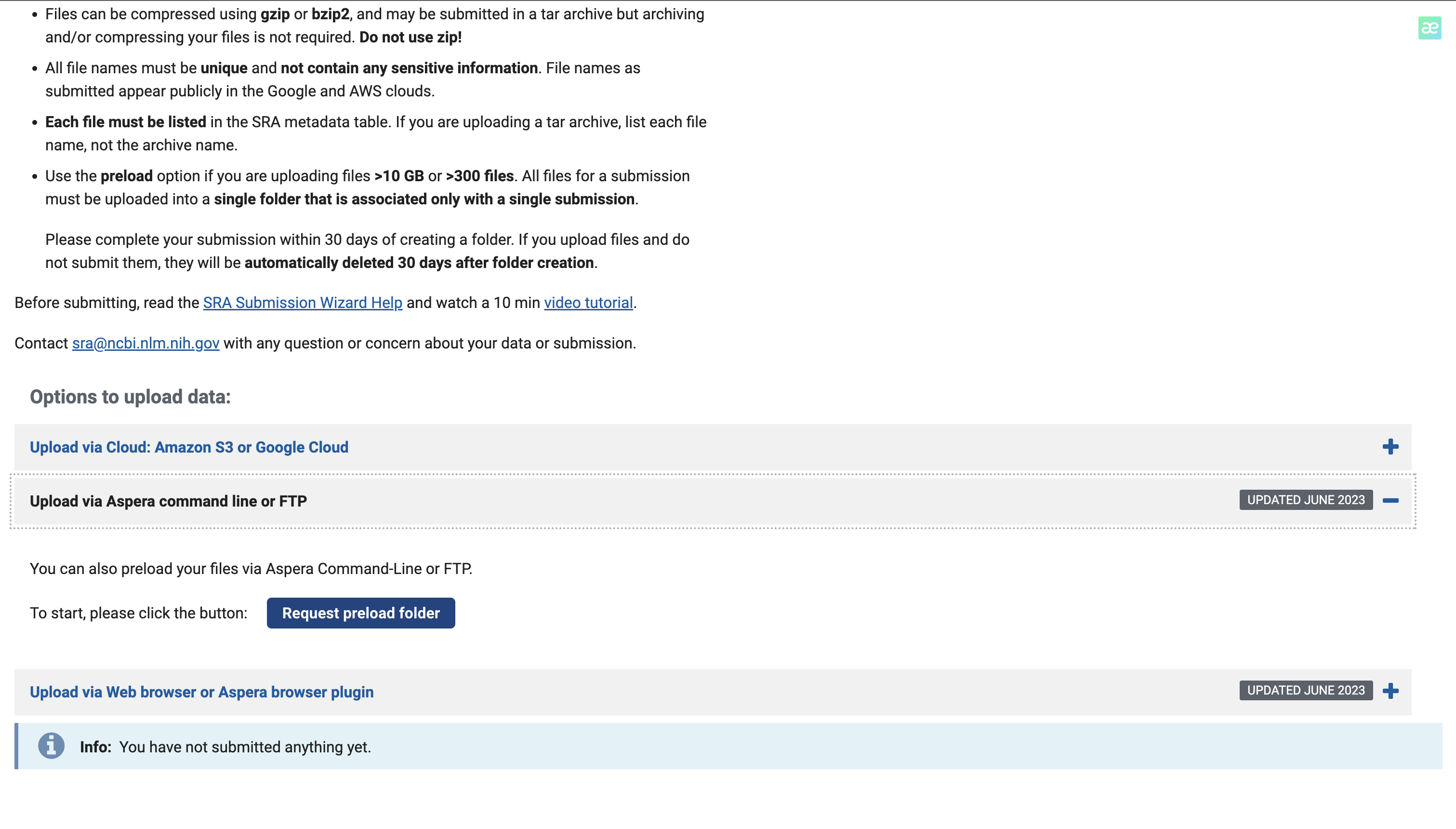
点击Request preload folder,ncbi提供了详细的上传教程
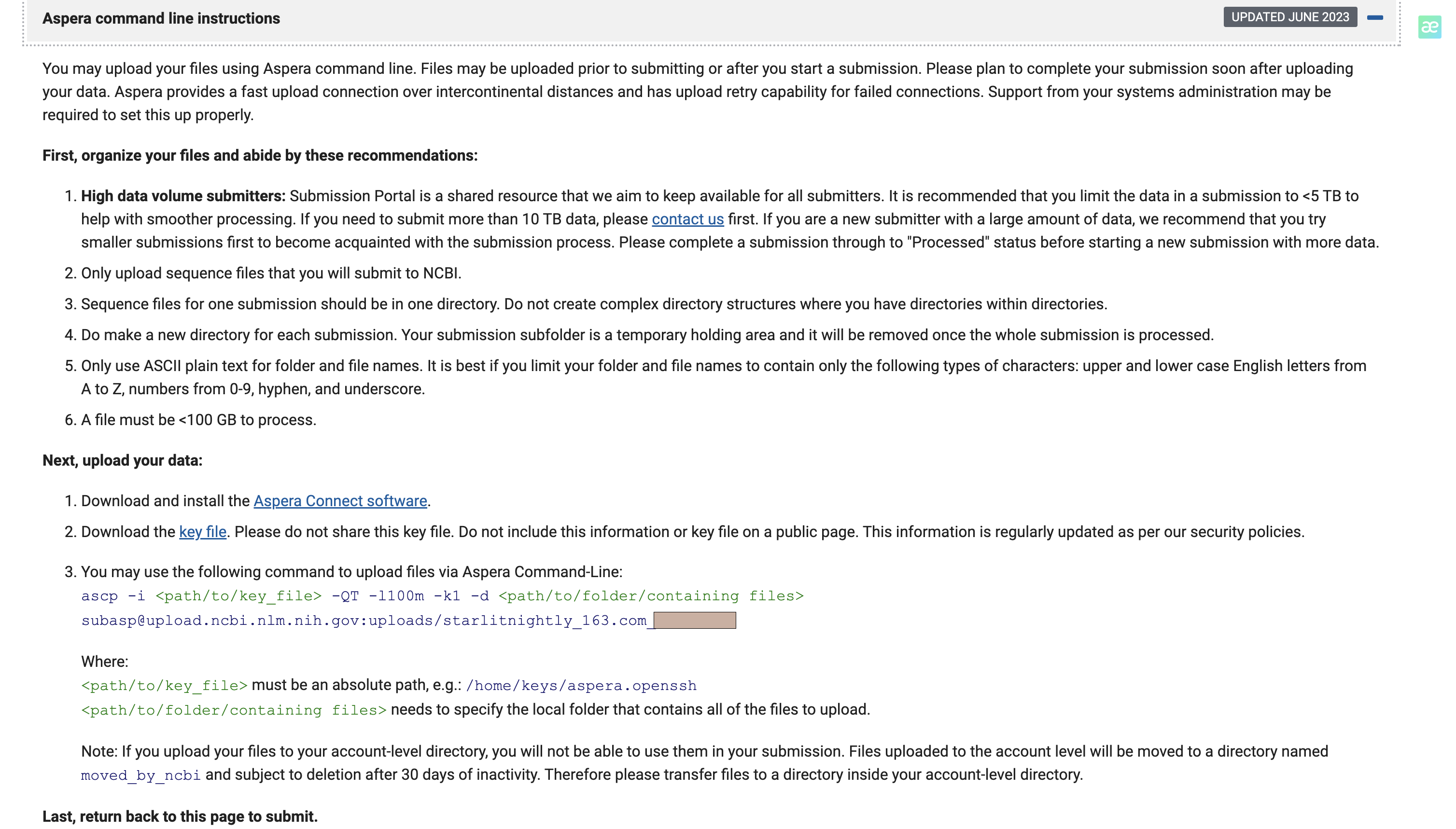
3.3 ascp环境安装
直接使用conda安装ascp,避免各种无意义的不兼容与报错。因为ascp的安装需要特定的glibc版本。
conda create -n ascp python=3.8
conda activate ascp
conda install -c hcc aspera-cli -y
ascp -h #检查安装
准备好ascp环境后,我们选择开始构建SRA项目
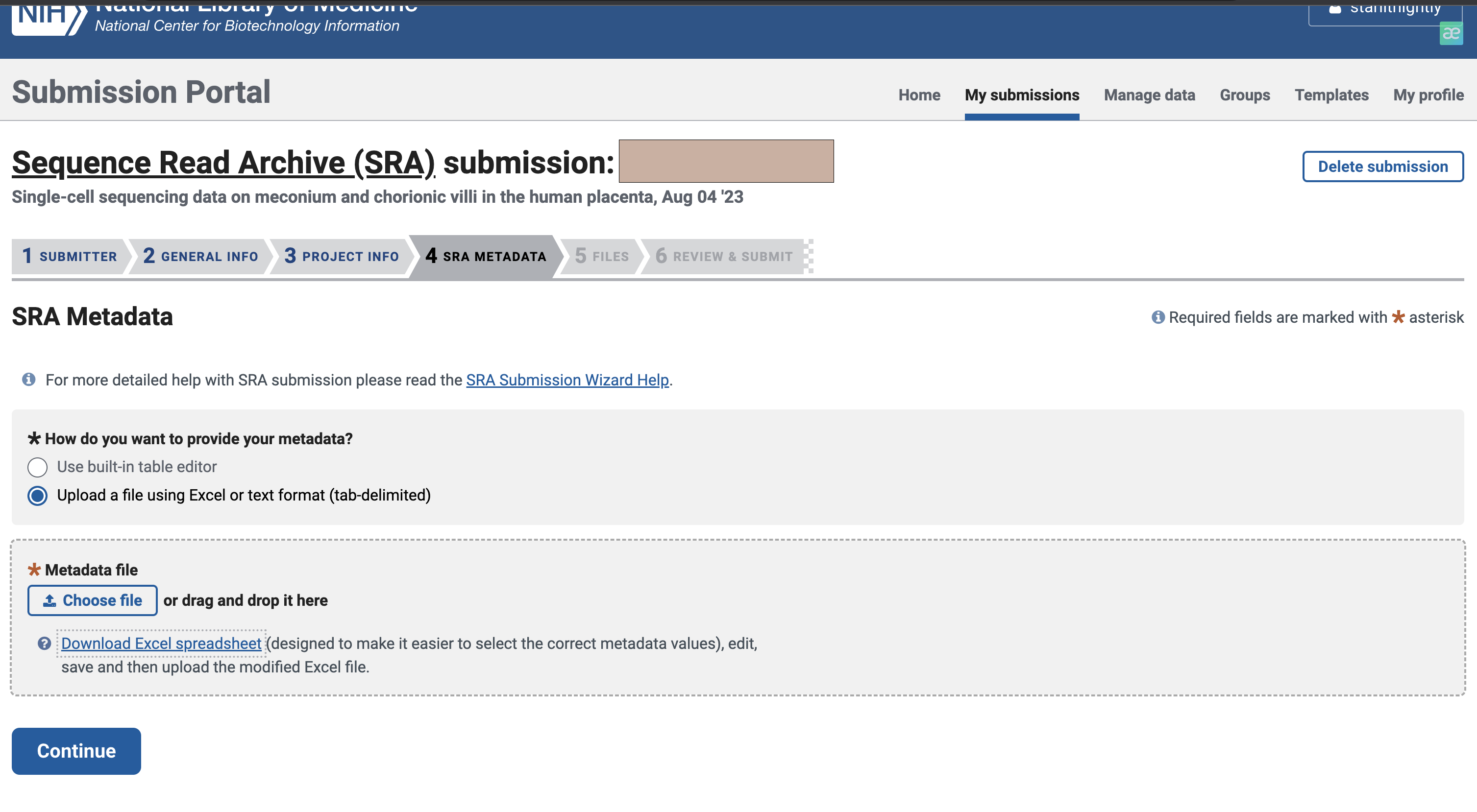
3.4 SRA上传内容填写
构建的过程比较简单,我们需要输入每一列所对应的信息即可,这里提供一个例子
| biosample_accession | library_ID | title | [library_strategy](#'Library and Platform terms'!A2) | [library_source](#'Library and Platform terms'!A27) | [library_selection](#'Library and Platform terms'!A36) | library_layout | [platform](#'Library and Platform terms'!A66) | instrument_model | design_description | filetype | filename | filename2 | filename3 | filename4 | filename5 | filename6 | filename7 | filename8 | assembly | fasta_file | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| SAMN36786*** | Name | RNA-seq of Homo sapiens: Decidua | RNA-Seq | TRANSCRIPTOMIC SINGLE CELL | RANDOM | paired | ILLUMINA | Illumina NovaSeq 6000 | Single cell 10X | fastq | ***_1_1_R1.fq.gz | ***_1_1_R2.fq.gz | ***_2_1_R1.fq.gz | ***_2_1_R2.fq.gz | ***_3_1_R1.fq.gz | ***_3_1_R2.fq.gz | ***_4_1_R1.fq.gz | ***_4_1_R2.fq.gz |
其中,你下载的excel里面有很多是可以选的,所以我加粗的才是需要自己填写而不法选择的。
- biosample_accession: 生物样本访问号
- library_ID: 库ID,这个是独一无二的,需要自己想好用什么ID存在SRA数据库
- title: 数据标题,这个标题就任意,但是一般规则是RNA-seq of 物种:组织
- library_strategy: 库构建策略,这里一般是RNA-seq
- library_source: 数据来源库,这里一般是TRANSCRIPTOMIC SINGLE CELL
- library_selection: 库选择方式,这里一般是RANDOM
- library_layout: 库布局,我这里是双端测序,所以写paired
- platform: 测序平台,我从测序公司给的文件里找到了Illumina
- instrument_model: 仪器模型,我从测序公司给的文件里找到了Illumina NovaSeq 6000
- design_description: 设计描述,我们是单细胞测序所以是Single cell 10X
- filetype: 文件类型,我们上传的文件类型,这里一般都是fastq
- filename: 文件名(第1个文件)一般一个单细胞文库最大是8个文件,双端测序的话最小是2个文件,大部分都是两个文件,取决于测序公司给你的结果。
- filename2: 文件名(第2个文件)
- filename3: 文件名(第3个文件)
- filename4: 文件名(第4个文件)
- filename5: 文件名(第5个文件)
- filename6: 文件名(第6个文件)
- filename7: 文件名(第7个文件)
- filename8: 文件名(第8个文件)
3.5 上传本地fastq
填好这个表后,我们点击continue,进入文件上传页面,跨洲际上传,这里只介绍ascp,以下命令是从官网复制的,切记不可照抄
ascp -i /mnt/home/zehuazeng/ncbi/aspera.openssh -QT -l100m -k1 -d /mnt/home/zehuazeng/media/207D/origData [email protected]:uploads/starlitnightly_163.com_***
这里需要修改的只有-i和-d两个参数,注意是绝对路径
- -i: openssh文件路径,这个是在上传页面有一个超链接可以下载
- -d: 需要上传的文件夹,里面只需要包含你要传的fq文件即可,文件名与前面填的filename1-8一致。
由于网络波动,所以我写了一个.sh文件,检测到上传失败可以自动重传,我们命名该文件为upload.sh
#!/bin/bash
while true; do
ascp -i /mnt/home/zehuazeng/ncbi/aspera.openssh -QT -l100m -k1 -d /mnt/home/zehuazeng/media/207O/origData8 [email protected]:uploads/starlitnightly_163.com_UFgOBYes
if [ $? -eq 0 ]; then
echo "Command completed successfully."
break
else
echo "Command failed. Retrying in 5 seconds..."
sleep 5
fi
done
然后在终端输入./upload.sh即可运行,注意文件需要先修改权限chmod 777 ./upload.sh。
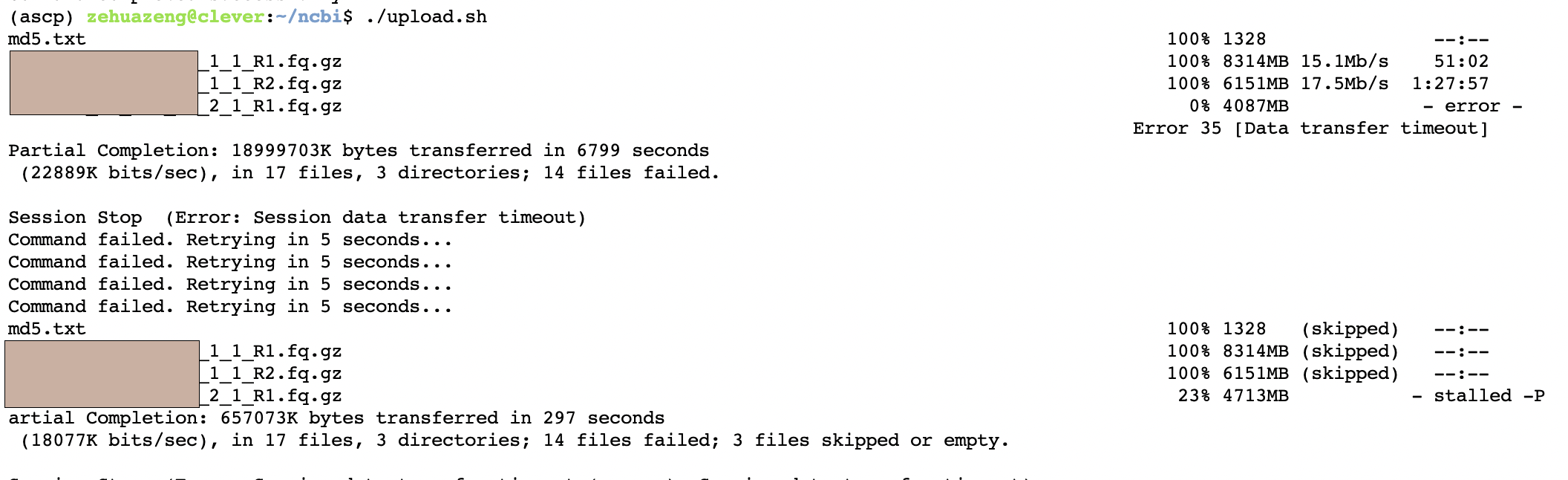
我们发现自动上传便开始了,并且会自动检测上传成功与失败。我们等全部文件上传好后,回到刚才的SUB页面
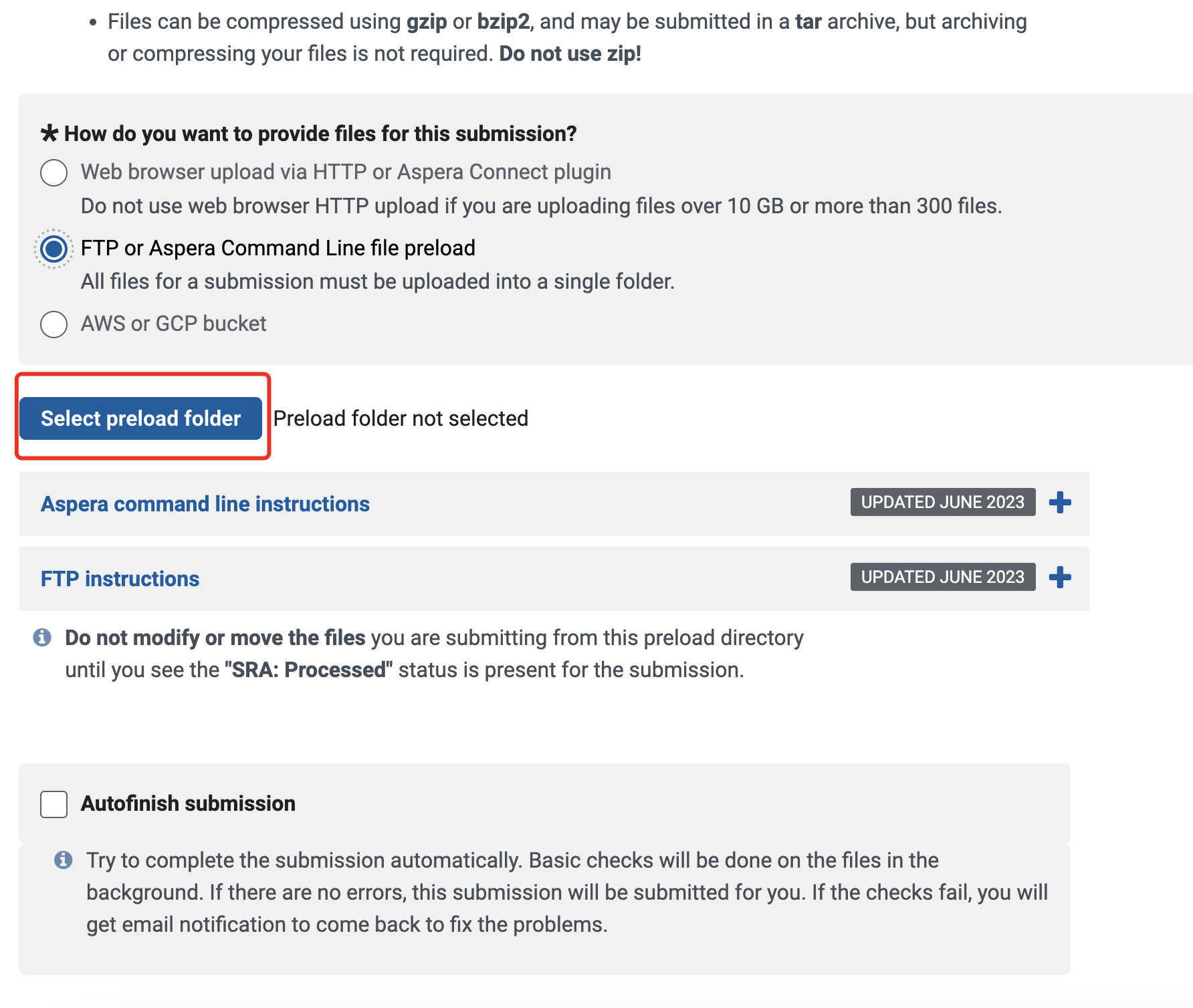
我们选择Select preload folder,这里origData7是我们已经传好的文件夹,而origData8是正在上传的文件夹
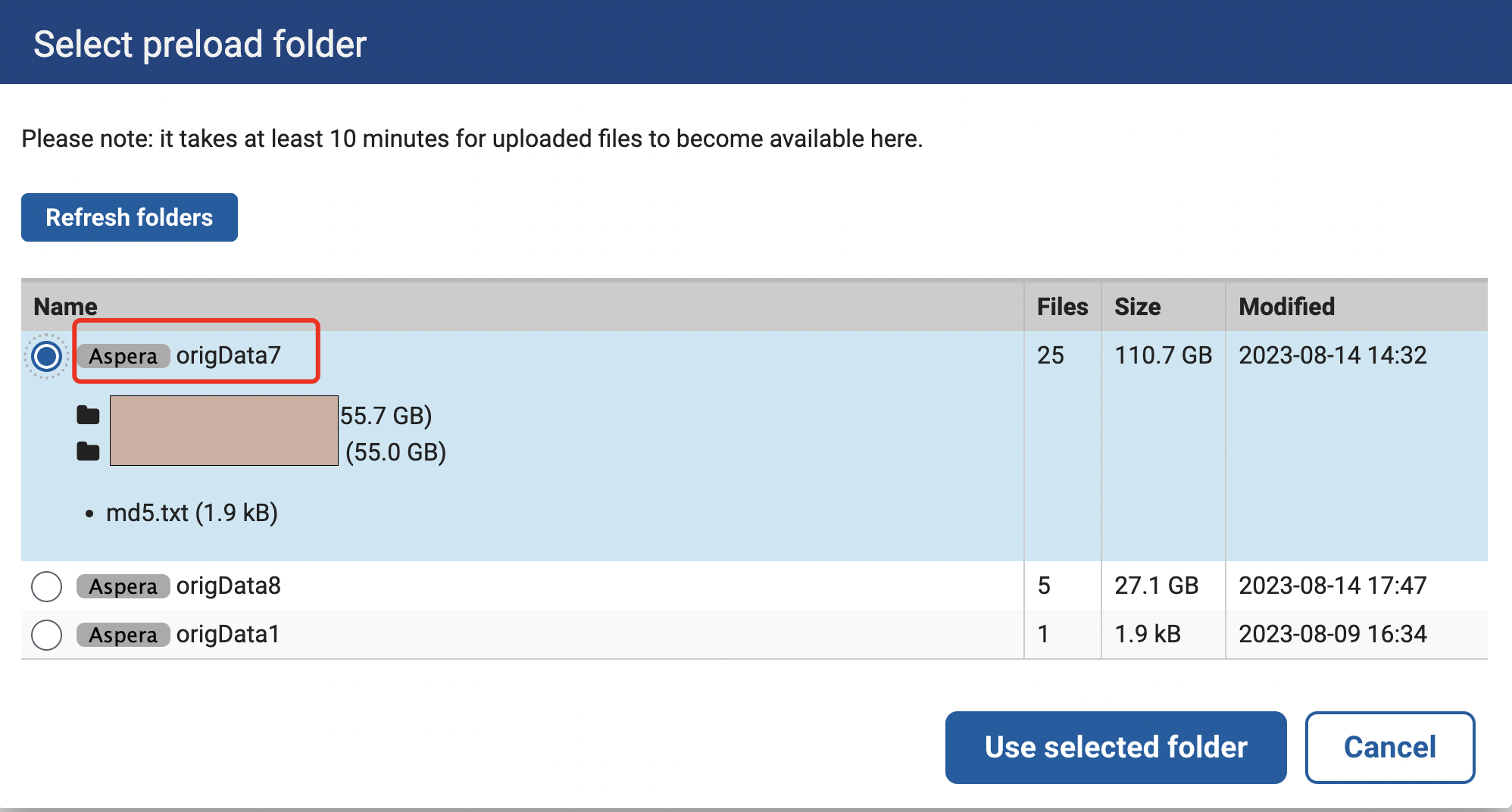
选择完了我们点击Continue,就会跳到最后一个页面,一般来说文件会自动帮你选出来,根据你前面填写的filename1-8
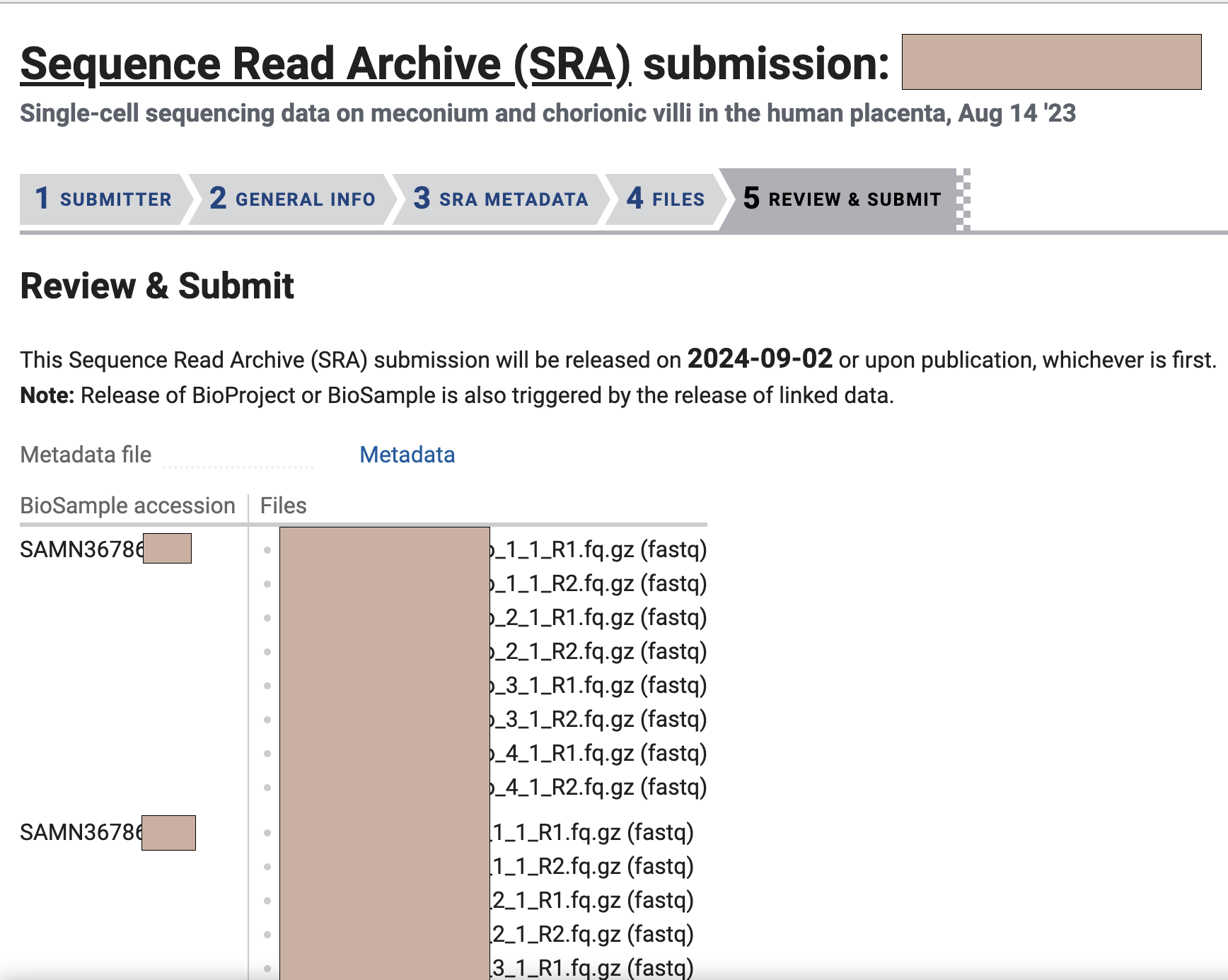
我们点击Submit就好了,会跳转到最开始的页面,提示我们正在处理中。
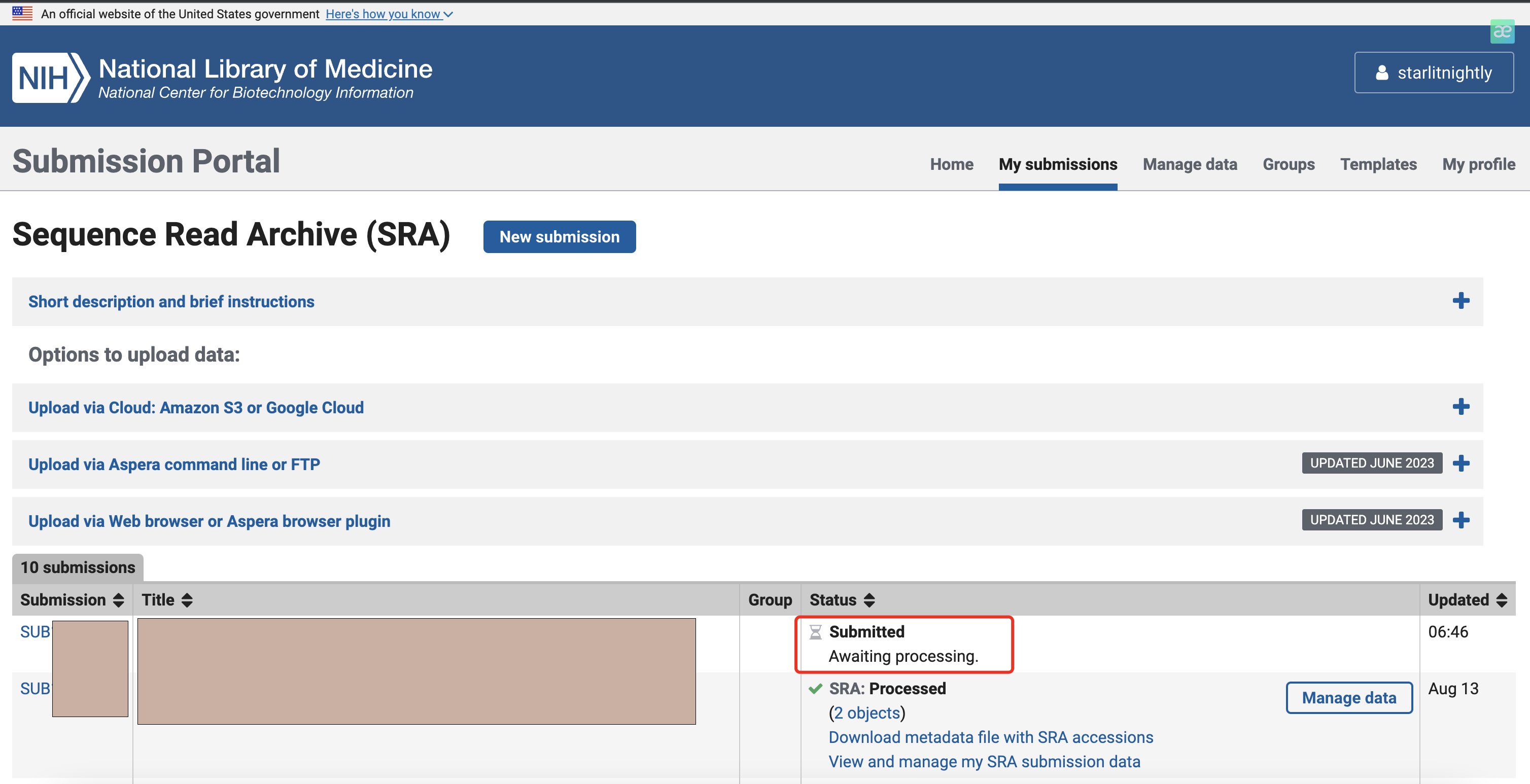
3.6 其他
我在上传的时候遇到了一次失败,报错提示是
2023-08-06T22:03:02 sra_subprocess error: Finished: /panfs/traces01.be-md.ncbi.nlm.nih.gov/trace_software/pipeline/sra_prod/transform_tools/sharq_load.py --config /panfs/traces01.be-md.ncbi.nlm.nih.gov/trace_software/pipeline/sra_prod/config.sra.public /panfs/traces01.be-md.ncbi.nlm.nih.gov/trace_software/pipeline/sra_prod/transform_tools/sharq --platform=ILLUMINA --log-level=info --output=/export/home/SSD/production_sra_public/sge1240.212826.trace.run_load.sh/SRR25541***.run_load/SRR25541***.output ***_3_1_R2.fq.gz ***_4_1_R2.fq.gz ***_2_1_R2.fq.gz ***_2_1_R1.fq.gz ***_1_1_R1.fq.gz ***_1_1_R2.fq.gz ***_3_1_R1.fq.gz ***_4_1_R1.fq.gz; pid=218120, rc=243
这种错误不是我能解决的,于是我写了封邮件发送到[email protected],然后过了两天再看邮箱,工作人员后台已经帮我弄好了。
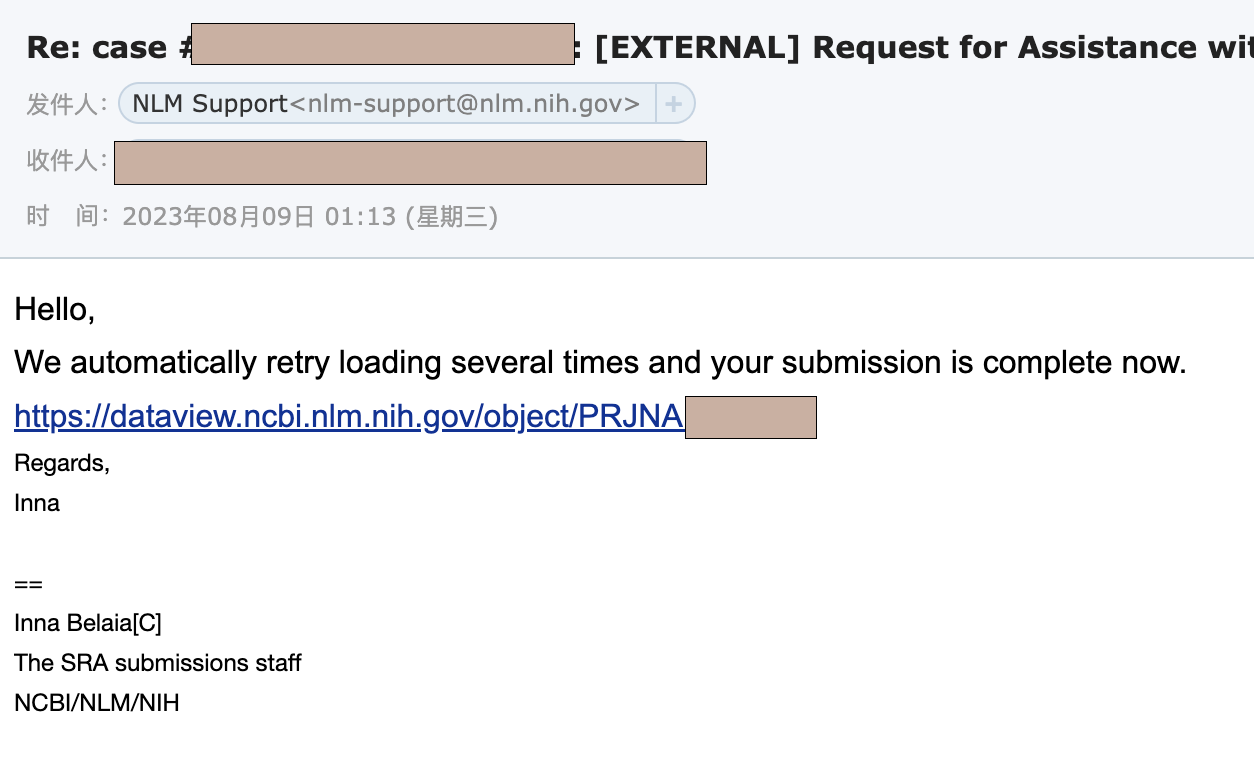
4. GEO上传
我们将原始数据成功上传到SRA数据库后,我们还需要上传处理后的数据到GEO数据库上。GEO数据库与SRA的上传有一些类似,但也有所区别。可能是由于处理后的文件通常不会太大,所以上传可以用ftp。
4.1 新建GEO提交
我们点击New Submission新建一个提交
我们选择high-throughout sequencing来完成scRNA-seq数据的上传,点开后发现,我们需要先下载一个meta文件进行信息的填写。
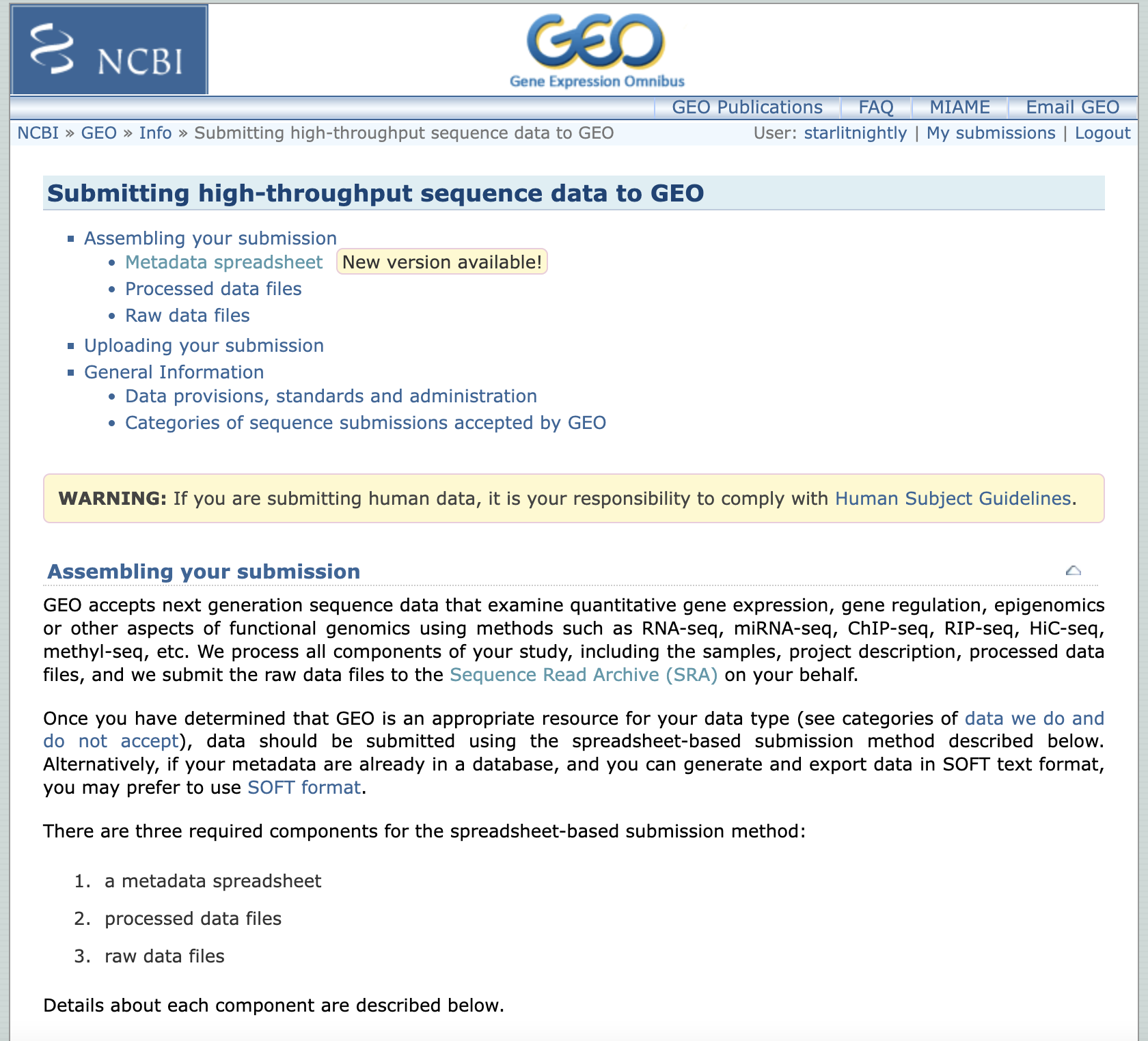
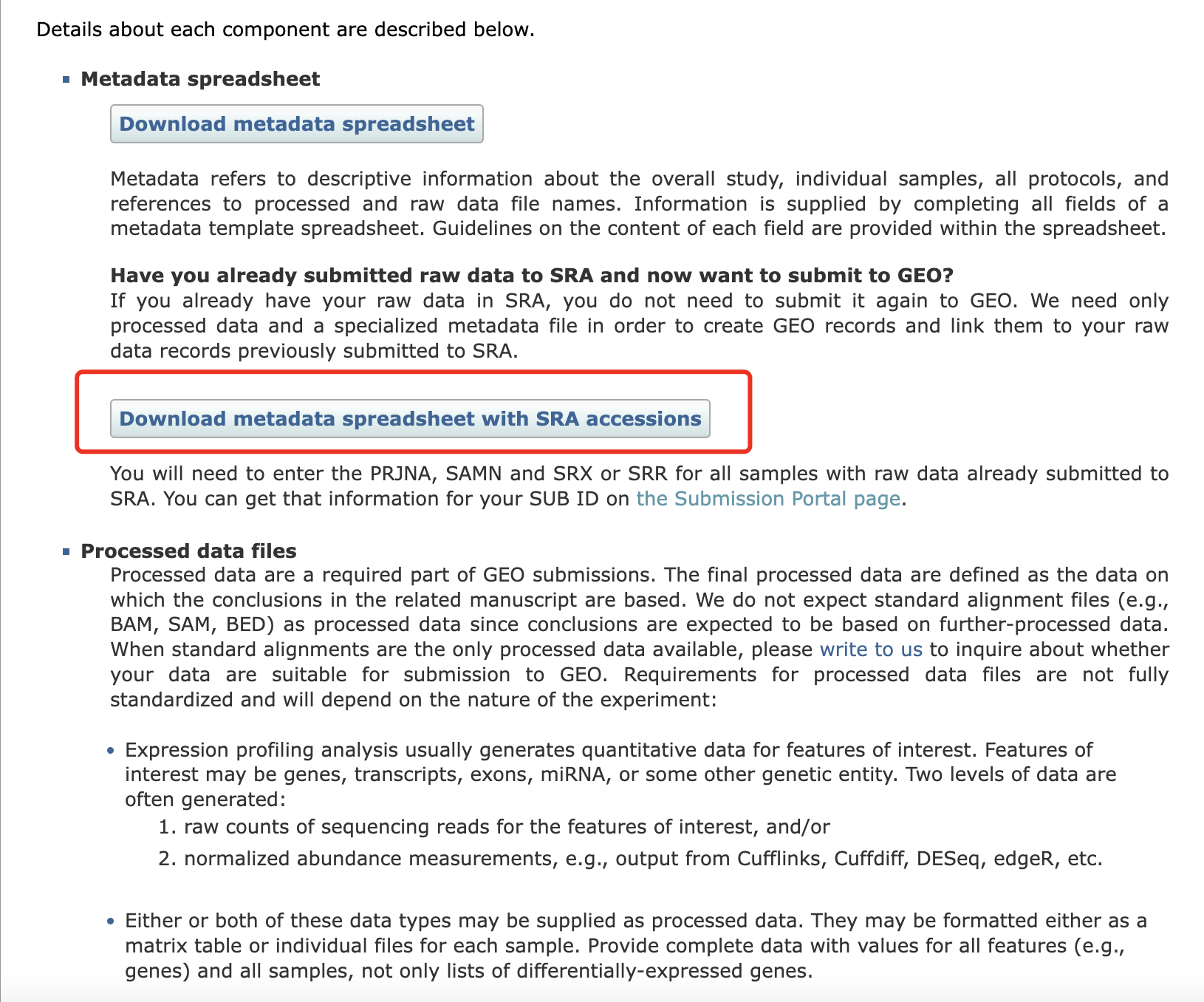
我们选择第二个,因为我们已经把测序文件上传到了SRA数据库,这样可以避免重复上传原始数据。
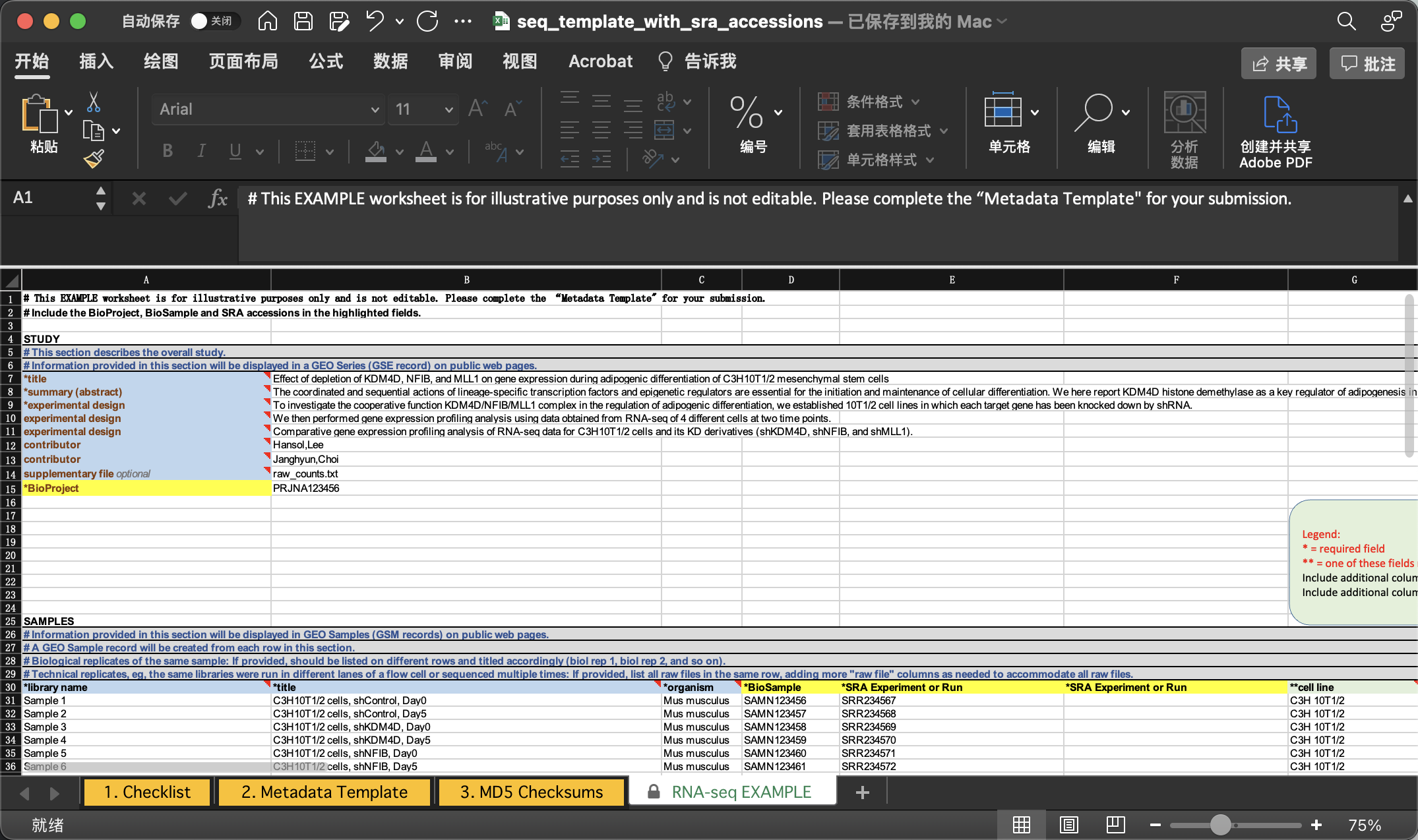
我们照着EXAMPLE的格式填写即可。
4.2 上传处理文件与meta
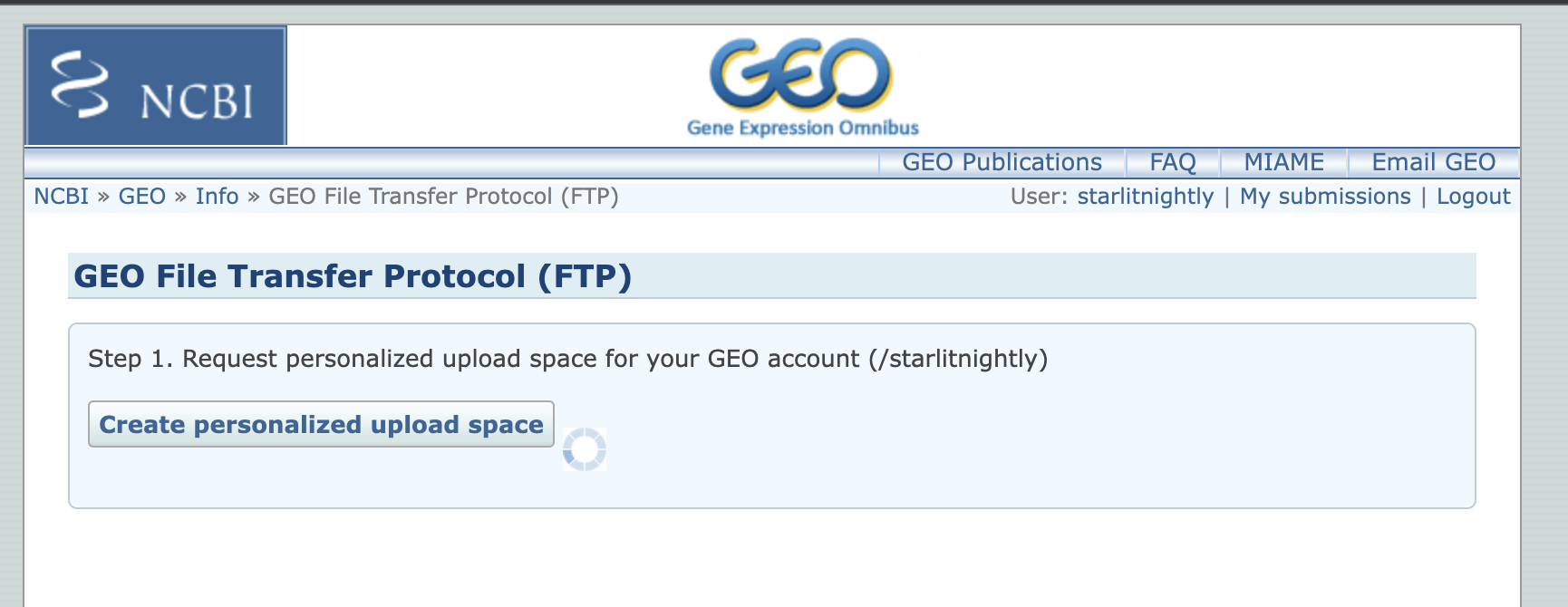
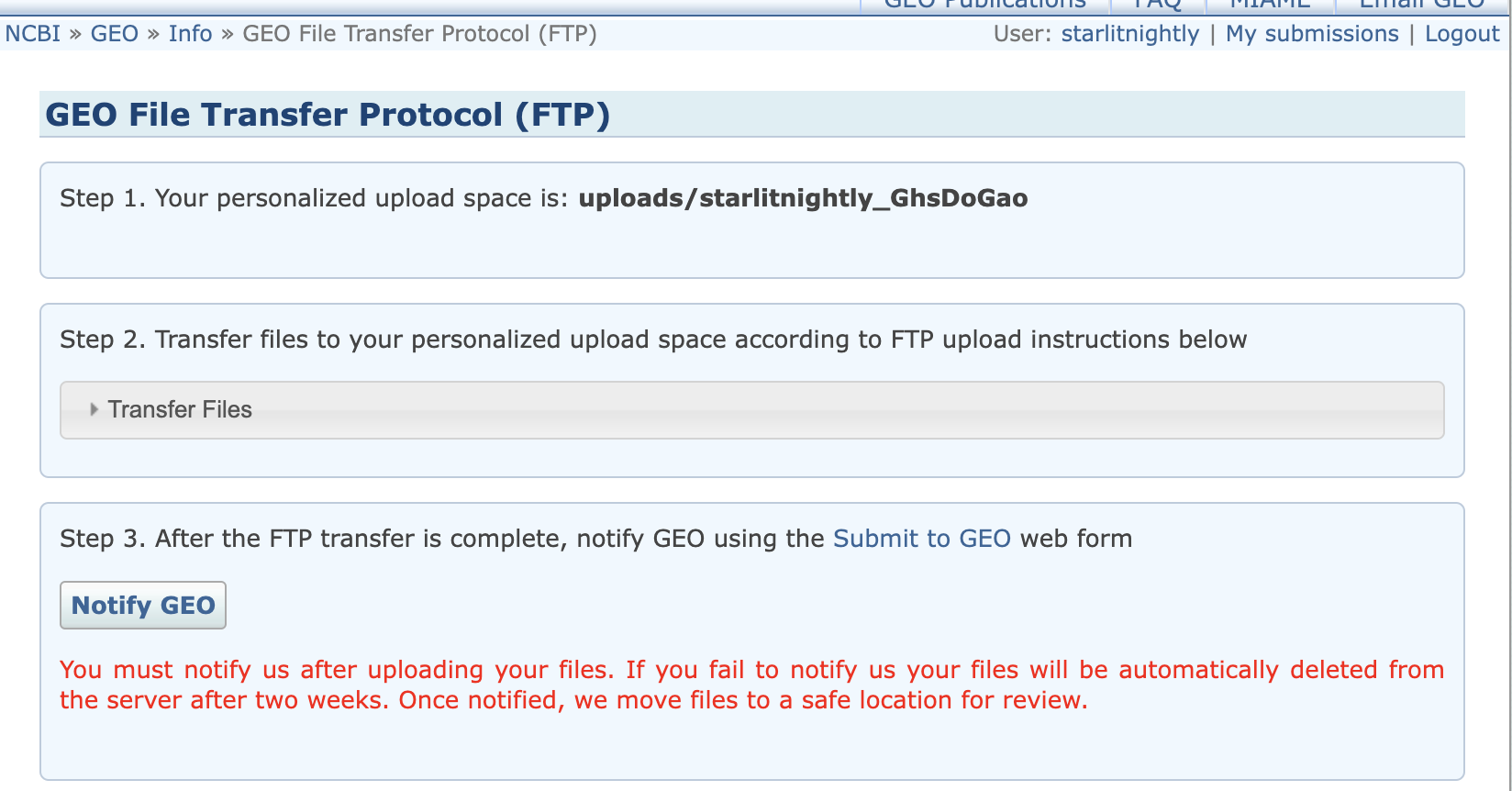
然后我们点击Create personalized upload space创建自己的ftp空间
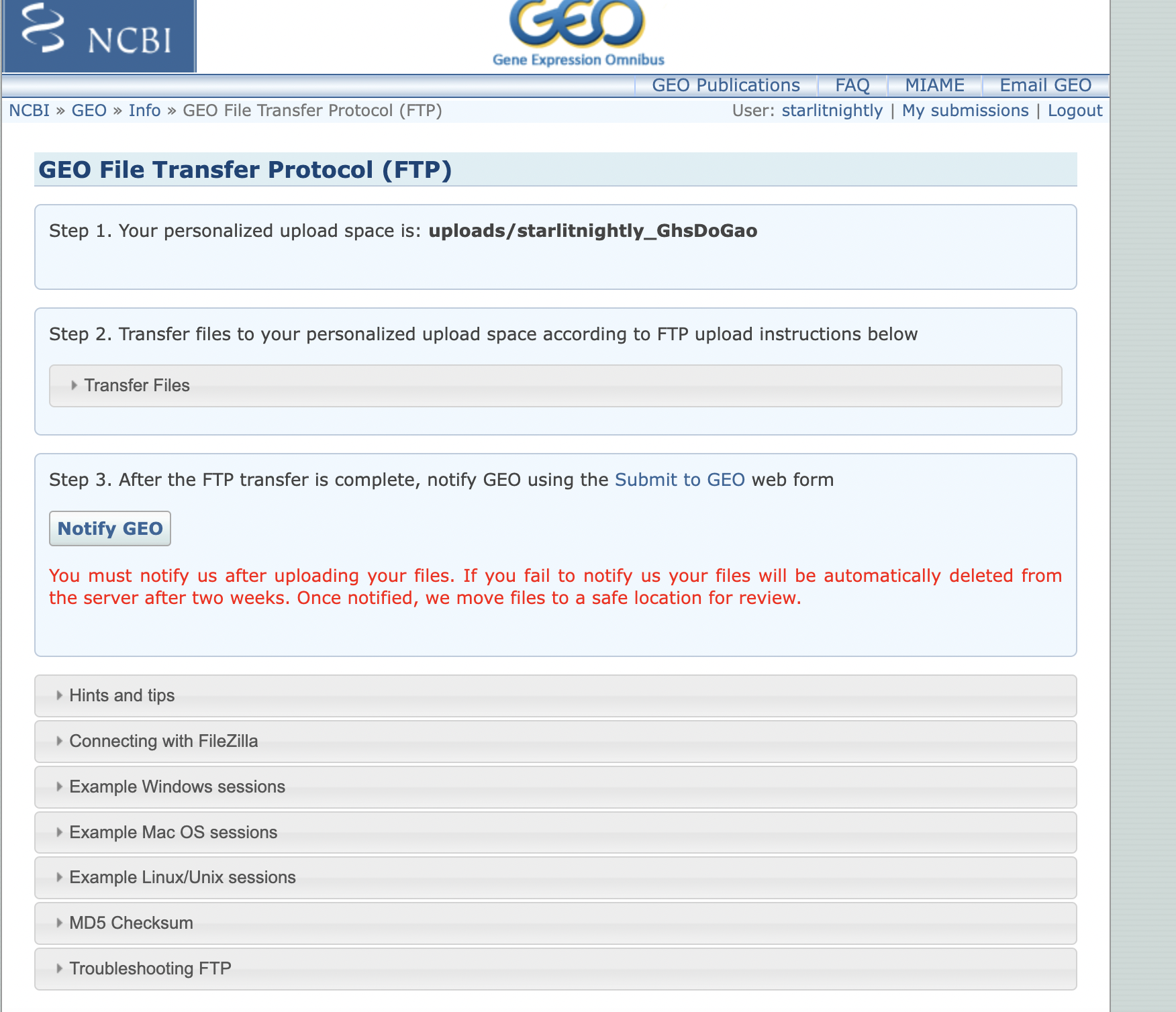
等待一会儿便会加载出Step 2,我们点击左边的箭头展开,会发现里面提供了GEO数据库的服务器信息。
- Host address:
- username
- password
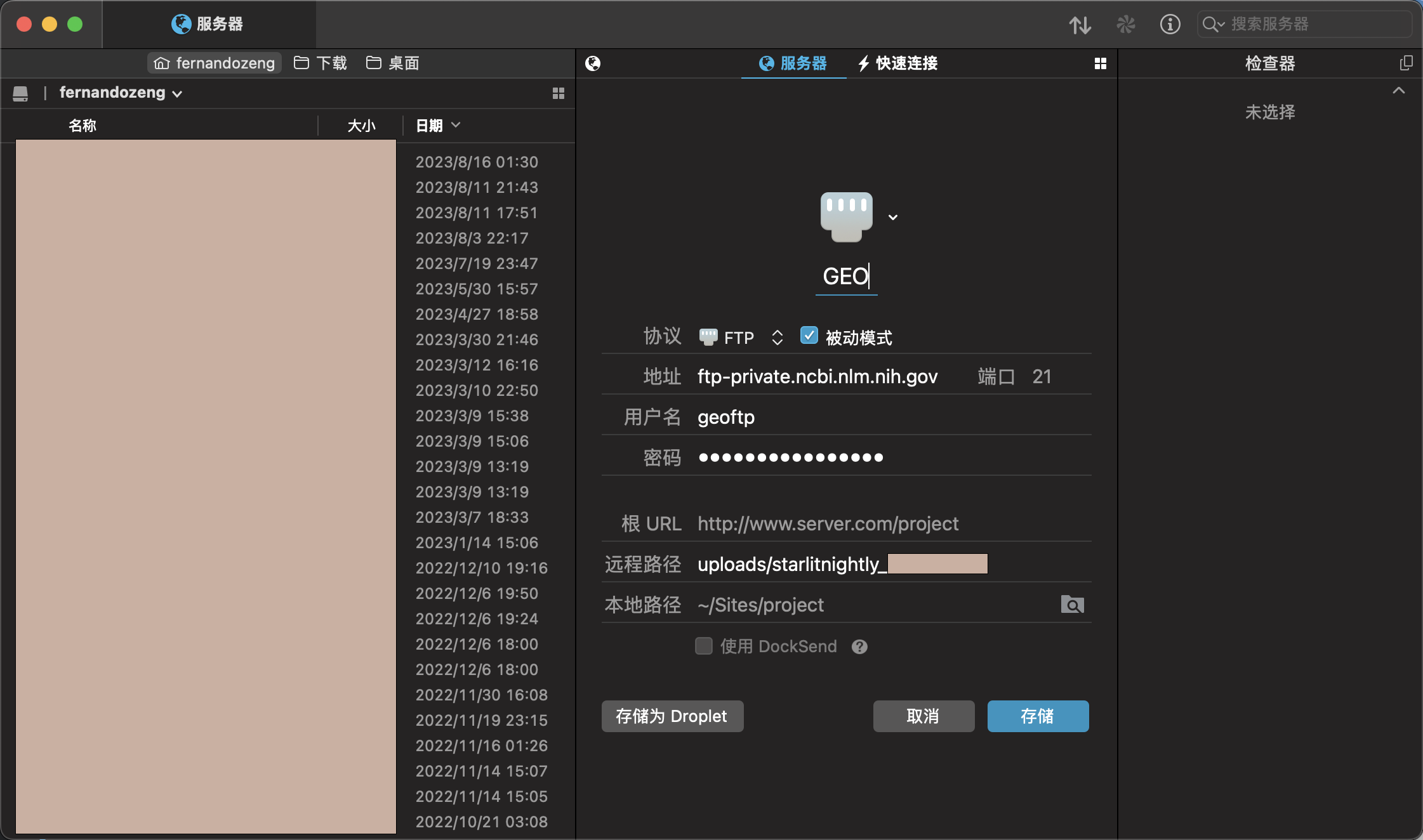
我们根据这三个信息可以连接到远程的GEO服务器上,但需要注意的是,我们连接的远程目录不能是默认的,而是uploads/starlitnightly_***这个在图中我用红色区域圈了起来

我是mac系统,所以我用transmit来做ftp文件传送,我们将刚才的Hostname填到地址,username填到用户名,password填到密码,同时设定远程路径为刚刚提到的uploads/starlitnightly_***
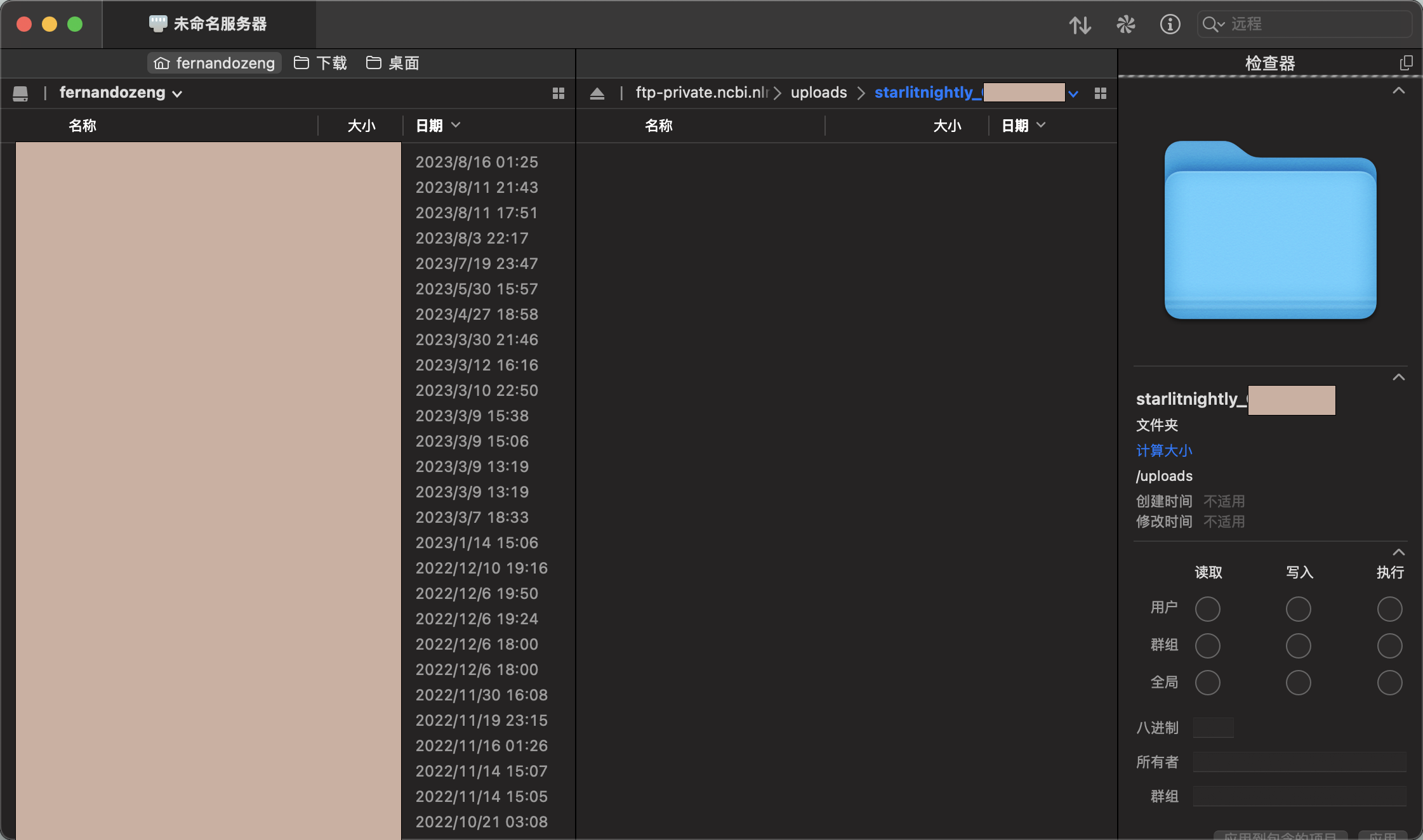
连接后我们会发现里面是空的,我这里需要传过滤后的h5文件以及velocyto生成的剪接/未剪接矩阵,所以我新建了两个文件夹,一个叫h5_file,一个叫loom_file,同时我在meta里面已经填写好了每一个样本对应的文件名
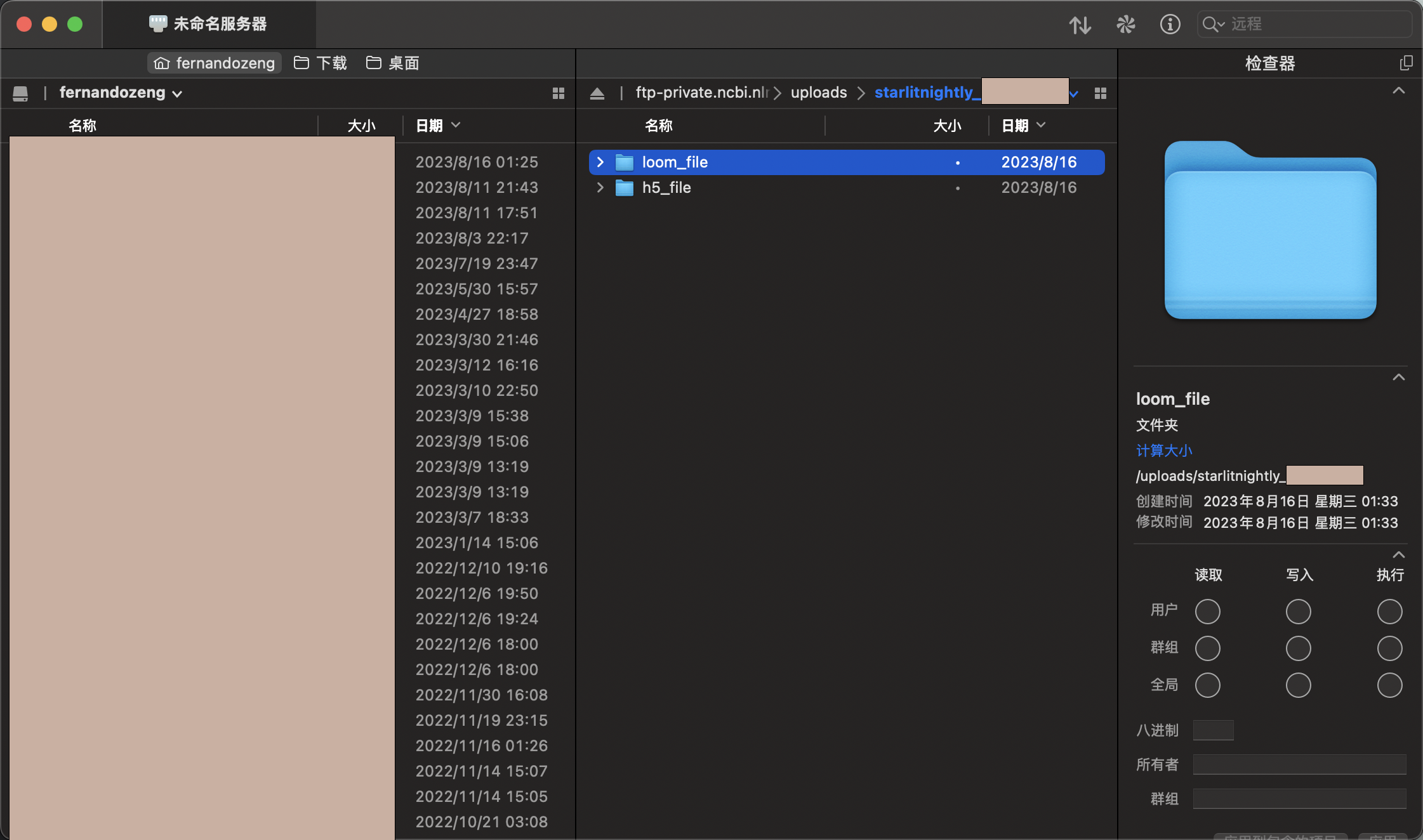
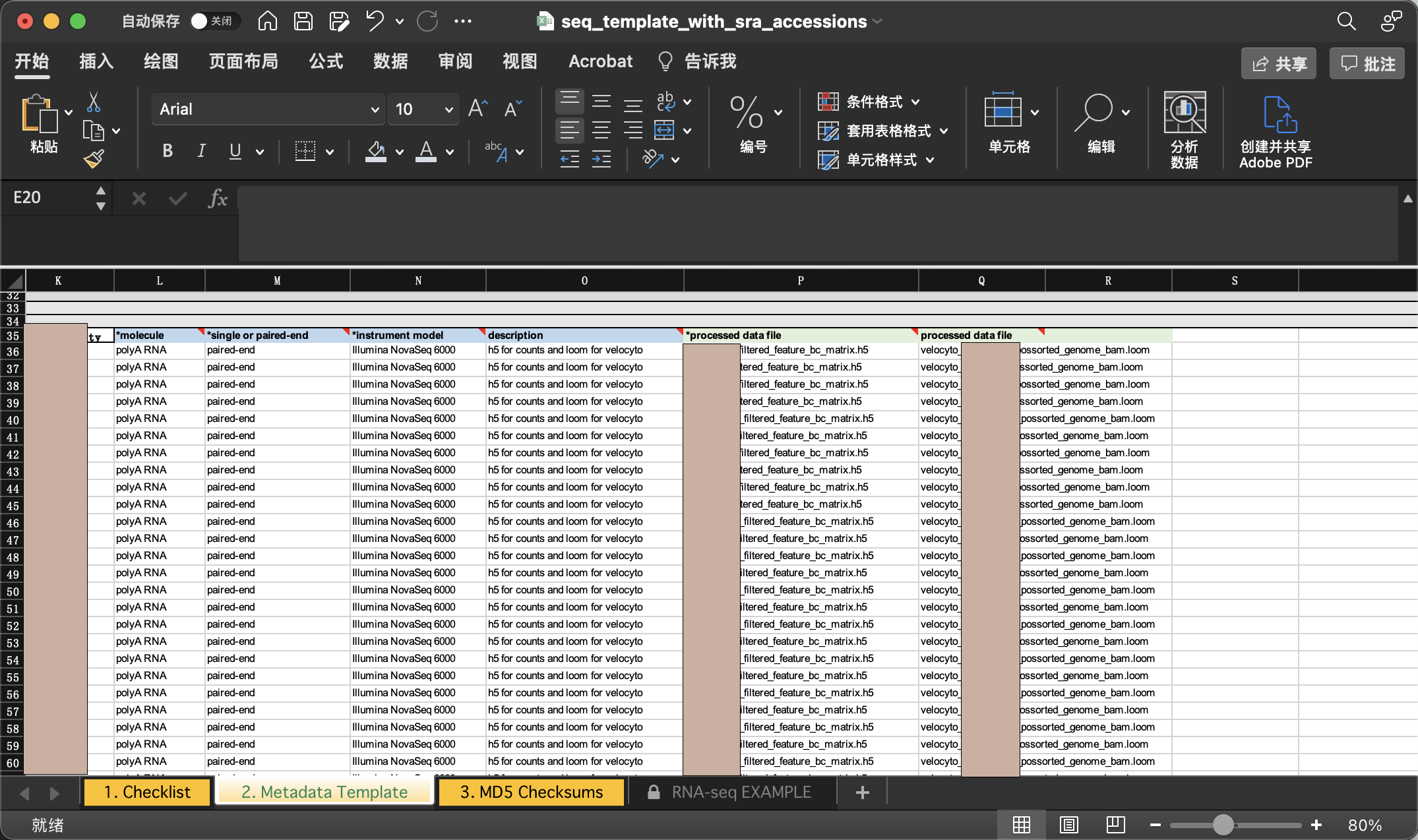
我们直接拖动文件进入对应文件夹即可上传。同时需要注意的是,meta文件也需要一并上传
4.3 提交GEO申请
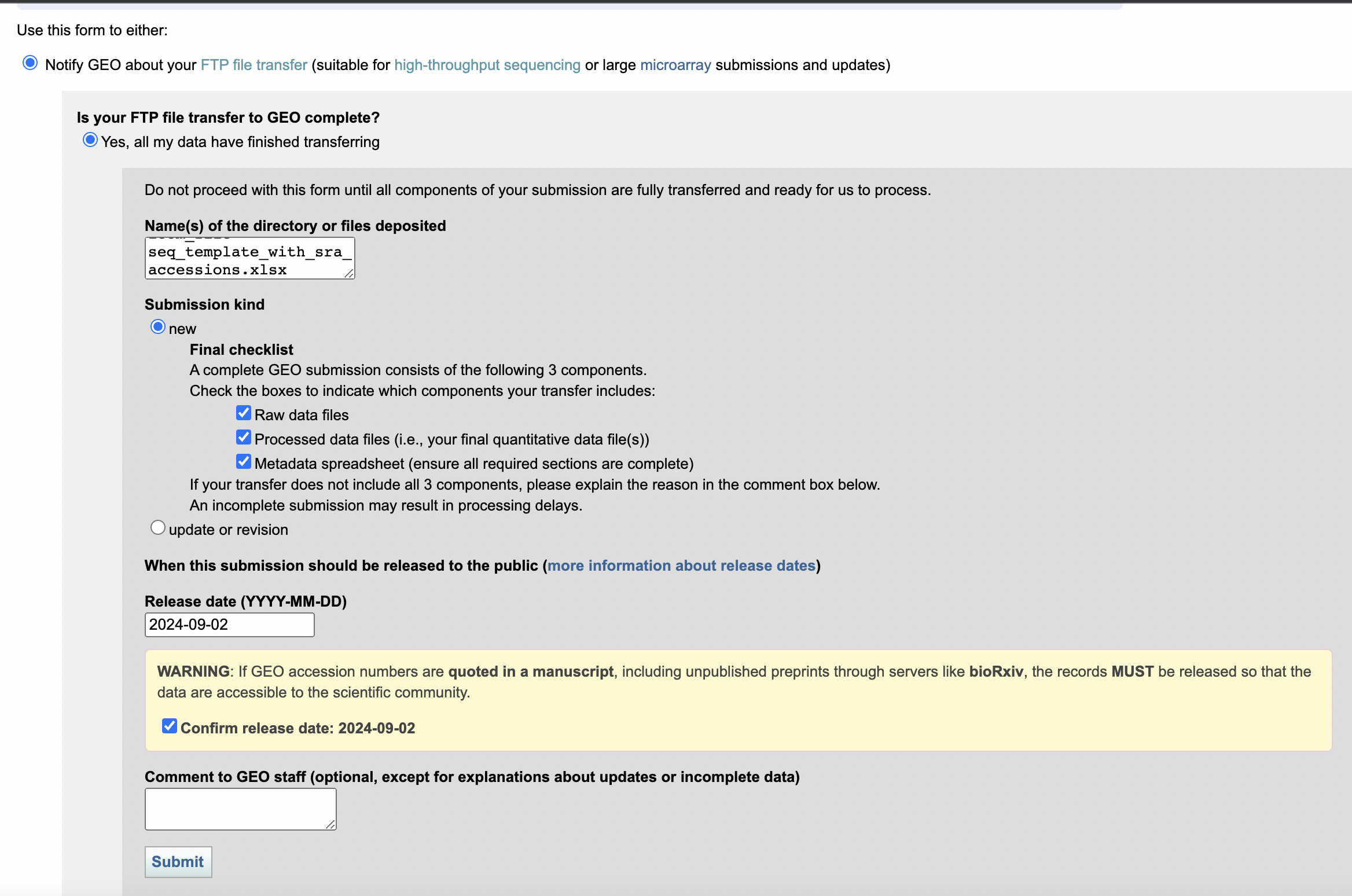
我们在传好文件后,回到GEO申请界面,点击Notify GEO,我们填写好目录和文件描述,点击submit即可。
4.4 确认GEO
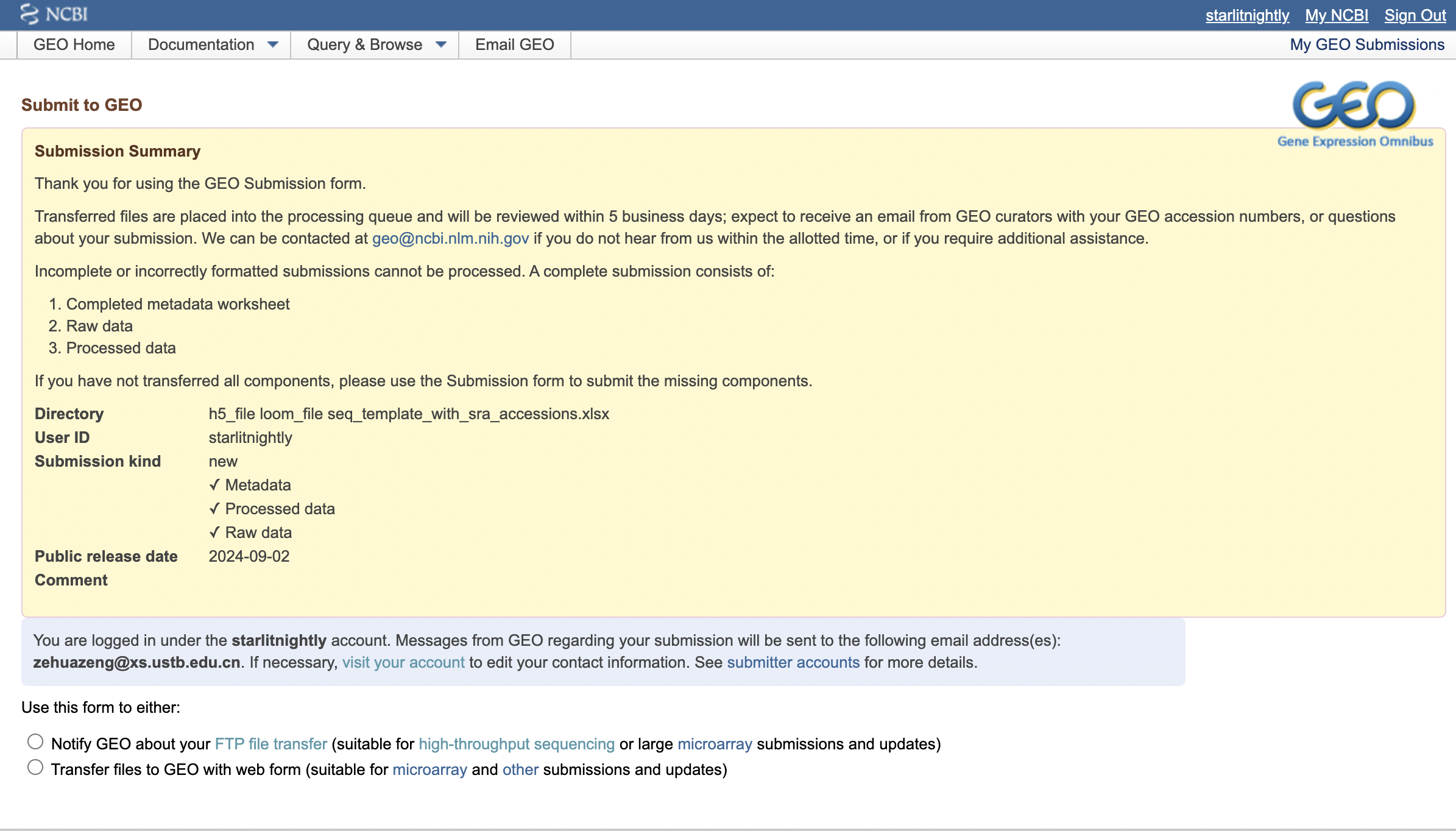
大概一天左右(工作日),你就会收到一封来自GEO工作人员的审核邮件,如果有问题会在邮件里说明,我这里没有问题就直接回道GEO里查看我的提交,发现确实多了一个记录。
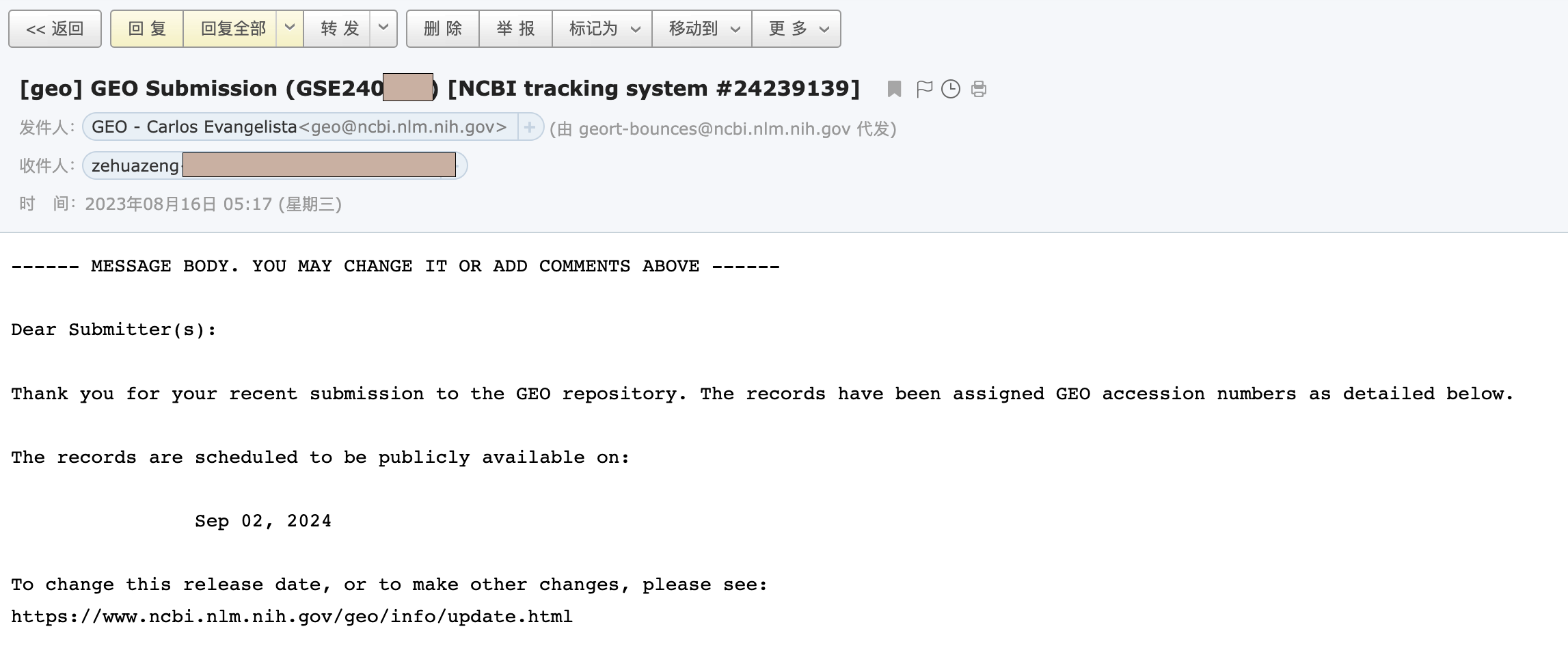
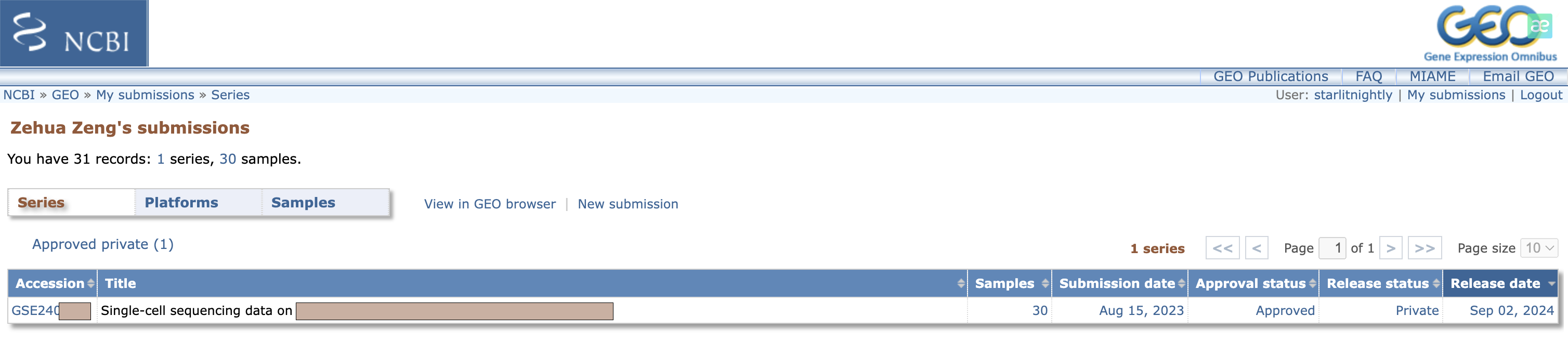
我们点进去后,可以点击Update更新一些相关信息。